Эффект SNP G.73467314G>A (SSC7) на признаки продуктивности и состояние конечностей свиней
Автор: Гетманцева Л.В., Костюнина О.В., Бакоев С.Ю., Форнара М.С., Карпушкина Т.В., Бакоев Н.Ф., Свеженцева Н.А., Колосова М.А.
Журнал: Вестник аграрной науки @vestnikogau
Рубрика: Сельскохозяйственные науки
Статья в выпуске: 4 (73), 2018 года.
Бесплатный доступ
Увеличение объёмов производства высококачественной конкурентоспособной и экологически безопасной продукции животноводства приобретает стратегическое значение для обеспечения продовольственной безопасности РФ. Повышенный интерес к улучшению продуктивных качеств свиней оказал значительное влияние на развитие молекулярно-генетических исследований в данном направлении. Целью данной работы было разработать методику для тестирования SNP g.73467314G>A и оценить его эффект на откормочные и мясные качества, а также на состояние конечностей у свиней крупной белой породы и ландрас. Материалом для исследования служили пробы биологического материала (ушные выщипы) хряков крупной белой породы (n=144) и породы ландрас (n=120), принадлежащие племенному предприятию ООО «Знаменский СГЦ». В результате разработанной тест-системы методом пиросеквенирования были определены три генотипа АА, AG и GG для варианта g.73467314G>A (SSC7) и установлена статистически значимая ассоциация (Р=0.003) между генотипами и состоянием задних конечностей у свиней породы ландрас. Наилучшие оценки задних конечностей имели свиньи, обладающие генотипом АА. Отсутствие связи между генотипом АА и признаками откормочной и мясной продуктивности позволит проводить отбор с учетом этого генотипа, не затрагивая ростовые и мясные показатели свиней. В исследуемой выборке свиней крупной белой породы частота минорного аллеля А составила 0.05, что свидетельствует об очень низком уровне полиморфизма. Таким образом, полученные результаты в нашей работе позволяют предположить, что вариант g.73467314G>A можно рассматривать в качестве генетического маркера состояния конечностей у свиней породы ландрас. Разработанная методика тестирования позволит провести дальнейшие исследования на большем поголовье свиней различных пород и кроссов, разводимых в племенных хозяйствах РФ.
Свиньи, откормочная и мясная продуктивность, конечности, тест-система
Короткий адрес: https://sciup.org/147230617
IDR: 147230617 | УДК: 619:575.22:[636.4.03+619:611.71:636.4] | DOI: 10.15217/issn2587-666X.2018.4.65
Effect SNP G.73467314G> A (SSC7) on productivity and leg conformation traits in pigs
The increase in the production of high-quality competitive and environmentally friendly livestock products is of strategic importance for ensuring Russia's food security. The increased interest in improving the productive qualities of pigs has had a significant impact on the development of molecular genetic studies in this direction. The purpose of this work was to develop a technique for testing SNP g.73467314G>A and to assess its effect on productivity and leg conformation traits in pigs of Large White (n=144) and Landrace (n=120) to the breeding enterprise of OOO Znamensky SGC, were used as the material for the study. As a result of the developed test system by pyrosequencing, three genotypes AA, AG and GG for variant g.73467314G> A (SSC7), and a statistically significant association (P=0.003) between the genotypes and hind legs conformation in the Landrace were established. The best estimates of the hind legs conformation were pigs with the AA genotype. The absence of a link between the AA genotype and traits of growth and meat productivity will allow selection based on this genotype, without affecting the growth and meat indicators of pigs. In the study sample of Large White pigs, the frequency of the minor allele A was 0.05, which indicates a very low level of polymorphism. Thus, the results obtained in our work suggest that the variant g.73467314G>A can be considered as a genetic marker of the state of hind legs conformation in the pigs of Landrace. The developed testing technique will allow further research on a larger number of pigs of different breeds and crosses in breeding farms of the Russian Federation.
Текст научной статьи Эффект SNP G.73467314G>A (SSC7) на признаки продуктивности и состояние конечностей свиней
Вве^ение. В современных условиях эффективное развитие свиноводства основано на интенсивных технологиях, позволяющих рационально использовать производственные мощности и значительно повысить продуктивность ^ивотных. Повышенный интерес к ростовым качествам свиней повлиял на развитие молекулярно-генетических исследований в данном направлении [1-3]. На сегодняшний день в базе данных Pig QTLdb (Pig Quantitative Trait Locus Database) идентифицировано 584 локуса для среднесуточного прироста свиней. Наибольшее количество локусов определено на хромосомах SSC1 (99 QTL), SSC4 (71 QTL) и SSC7 (57QTL).
В последнее время так^е мо^но отметить рост исследований, направленных на поиск локусов, ассоциированных с репродуктивными показателями [4-6]. По результатам полногеномных исследований на начало 2018 г. в базе данных «PigQTLdb» зарегистрировано 204 локуса для общего количества поросят при ро^дении, из них 157 локусов обнару^ены у свиней китайской породы эрхуалян и 47 у свиней европейских пород. В работе He L.C. с соавторами [7] у свиней породы эрхуалян значимые SNPs, ассоциированные с общим количеством поросят при ро^дении, определены на хромосомах SSC2 (rs81367039), SSC7 (rs80891106), SSC8 (rs81399474), SSC12 (rs81434499), SSC14 (rs80938898). Интересно отметить, что SNP rs80891106 (g.73467314G>A), располо^енный на SSC7 в позиции 73,5 Мbp был обнару^ен в области хромосомы, где ранее не были определены гены-кандидаты или QTL для плодовитости свиней. Сопоставив локализацию SNP rs80891106 с данными по раннее аннотированным QTL на SSC7, мы определили, что он располо^ен в локусах, идентифицированных для среднесуточного прироста (QTL, регион 0,0120,9 Mbp) [8], толщины шпика (50,3-120,7 и 55,9-101,2) [9, 10] и массы окорока (30,8-94,4) [11].
Цель иссле^ований – разработать методику для тестирования SNP g.73467314G>A и оценить его эффект на откормочные и мясные качества, а так^е на состояние конечностей у свиней крупной белой породы и ландрас, разводимых в племенном хозяйстве РФ.
Услови^, материалы и мето^ы . Исследования были выполнены в лаборатории молекулярных основ селекции Федерального государственного бюд^етного научного учре^дения «Федеральный научный центр ^ивотноводства – ВИЖ имени академика Л. К. Эрнста» в рамках выполнения задания Федерального агентства научных организаций (Ф^НО) №^^^^-^18-118021590138-1. Материалом для исследования слу^или пробы биологического материала (ушные выщипы) хряков крупной белой породы (n=144) и породы ландрас (n=120), принадле^ащие племенному предприятию ООО «Знаменский СГЦ». Все исследуемые ^ивотные были одного года ро^дения и имели одинаковые условия содер^ания и кормления. При дости^ении 100 кг свиней оценивали по следующим признакам: среднесуточный прирост (г), толщина шпика (мм), глубина мышечного глаза (мм), оценка передних и задних конечностей. Экстерьерную оценку ^ивотных проводили на ровной площадке, оценивали общий вид, конституцию, пропорциональность телосло^ения, и отдельные стати. Передние и задние конечности у свиней дол^ны быть прямыми, отвесно и широко поставленными, обеспечивать хорошую подви^ность ^ивотных. Узкая, иксообразная, слоновая или саблистая постановка ног считается большим пороком.
Для проведения молекулярно-генетических исследований геномную ДНК выделяли при помощи набора «ДНК-экстран-2» (НПО «Синтол», Россия) согласно рекомендациям производителя. Специфические олигонуклеотидные праймеры для идентификации SNP g.73467314G>A методом пиросеквенирования подбирали с помощью программ Primer-BLAST (NCBI). По результатам молекулярно-генетических исследований рассчитывали частоту аллелей и генотипов. Для расчета эффекта SNP на признаки продуктивности использовали однофакторный дисперсионный анализ. В качестве фактора выступал SNP g.73467314G>A, число градаций соответствовало числу генотипов. Согласно данному анализу, эффект существует, если F-рассч.>F-табл. при соответствующей степени достоверности.
Результаты и обсу^^ение. Разработанная тест-система предусматривает амплификацию фрагмента длиной 332 п.н., содер^ащего SNP g.73467314G>A с последующим пиросеквенированием. Полученные результаты показали, что в исследуемой выборке свиней крупной белой породы частота минорного аллеля ^ составила 0,05, что свидетельствует об очень низком уровне полиморфизма, практически об его отсутствии (табл. 1). Более 90% свиней крупной белой породы имели генотип GG. У свиней породы ландрас наоборот, минорным определен аллель G, но с достаточно высокой частотой (0,34), что проявилось в наличии трех генотипов ^^, AG и GG с частотами 45,0; 41,7 и 13,3% соответственно.
Tаблица 1 – Частоты аллелей и генотипов SNP g.73467314G>A у свиней крупной белой породы и ландрас
|
Порода |
Частота аллелей |
Частота генотипов, % |
|||
|
A |
G |
AA |
AG |
GG |
|
|
Крупная белая |
0,05 |
0,95 |
0,00 |
9,70 |
90,30 |
|
Ландрас |
0,66 |
0,34 |
45,00 |
41,70 |
13,30 |
По результатам однофакторного дисперсионного анализа статистически значимый эффект варианта g.73467314G>A установили только на состояние задних конечностей у свиней породы ландрас, уровень достоверности которого составил P=0,003 (табл. 2). Эффект генотипов на другие исследуемые признаки при уровнях достоверности Р≤0,05 в выборках свиней крупной белой породы и ландрас не установлен.
В изучаемой выборке свиньи породы ланрас, имеющие генотип ^^, обладали лучшей оценкой задних конечностей, по сравнению с ^ивотными с генотипом GG. Согласно полученным данным, мо^но предполо^ить, что поло^ительный эффект генотипа ^^ проявляется только в породе ландрас. Следует отметить, у свиней крупной белой породы генотип ^^ не был определен, а генотип AG имел очень низкую частоту, что возмо^но связано с особенностями генетических структур свиней крупной белой породы и ландрас.
Tаблица 2 – Эффект SNP g.73467314G>A на признаки продуктивности и состояние конечностей свиней
|
Признаки |
Генотипы |
P |
||
|
AA | |
AG 1 |
GG |
||
|
Крупная белая порода (n=144) |
||||
|
Среднесуточный прирост |
- |
870,42±18,69 |
922,29±10,38 |
0,115 |
|
Tолщина шпика |
- |
12,07 ± 0,59 |
10,66 ± 0,30 |
0,093 |
|
Глубина мышечного глазка |
- |
66,28 ± 2,87 |
62,45 ± 0,59 |
0,071 |
|
Оценка передних конечностей |
- |
3,71 ± 0,18 |
3,40 ± 0,06 |
0,110 |
|
Оценка задних конечностей |
- |
3,28 ± 0,18 |
3,40 ± 0,06 |
0,531 |
|
Ландрас (n= |
120) |
|||
|
Среднесуточный прирост |
902,62±15,32 |
904,36±17,37 |
832,00±29,61 |
0,086 |
|
Tолщина шпика |
12,86 ± 0,51 |
12,77 ± 0,45 |
13,14 ± 0,91 |
0,938 |
|
Глубина мышечного глазка |
59,84 ± 1,11 |
61,32 ± 1,34 |
59,56 ±0,56 |
0,549 |
|
Оценка передних конечностей |
3,44 ± 0,09 |
3,26 ± 0,09 |
3,14 ± 0,14 |
0,169 |
|
Оценка задних конечностей |
3,48 ± 0,09 |
3,17 ± 0,08 |
2,85 ± 0,14 |
0,003 |
Предполо^ить биологическую функцию исследуемого SNP g.73467314G>A (SSC7) довольно сло^но, т.к. он располо^ен в некодирующей области ДНК. По данным Pig QTLdb в непосредственной близости от него находятся гены RF00001(73234200..73234325) и ENSSSCG00000032058 (73861910..73911853), кодирующие рибосомную РНК и длинную некодирущую РНК соответственно.
На основании наших результатов, показывающих эффект SNP g.73467314G>A на состояние задних конечностей, мы проанализировали располо^ение локусов на SSC7, аннотированных раннее при изучении ассоциаций с постановкой конечностей и их дефектами. По данным базы Pig QTLdb на SSC7 было идентифицировано 5 локусов, ассоциированных с передними конечностями (FRLEGC) [12-14], 6 локусов с задними конечностями (HLEGC) [13-16], один локус с остеохондрозом (OSTEO) [15] и один с вро^денным недоразвитием мышц ног (SPLEG) (рис. 1). Ни один из этих локусов не находится в непосредственной близости (в районе 1 Mbp) от изучаемого нами SNP g.73467314G>A. В данном контексте следует подчеркнуть, что нами так^е не был установлен эффект SNP g.73467314G>A на толщину шпика и среднесуточный прирост, несмотря на располо^ение исследуемого полиморфизма в районе локусов, ассоциированных с этими признаками. Вероятно, это связано с особенностями генетической структуры и неравновесием по сцеплению у исследуемых популяций.
QTL Mapper и.2.019
о -rSW2564
-SW1873
-SW1354
■SWR1078
•SW1369
■SW472
■S0102
80 - SWR18O6
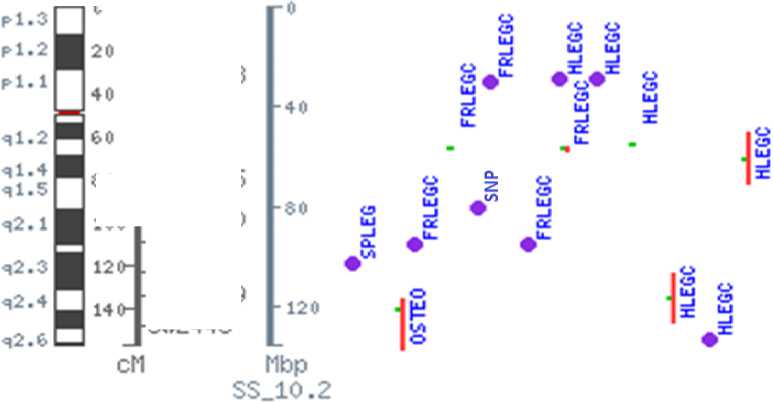
Рисунок 1 – Локусы, ассоциированные с состоянием и развитием конечностей свиней, располо^енные на SSC7 (по данным QTLdbPig): FRLEGC – постановка передних конечностей; HLEGC – постановка задних конечностей;
OSTEO – остеохондроз; SPLEG – вро^денное недоразвитие мышц;
SNP – вариант g.73467314G>A
ioo4TPS271O
-SW1083
-SW581
•TPS2699
•SW2446
Tаким образом, полученные результаты в нашей работе позволяют предполо^ить, что вариант g.73467314G>A мо^но рассматривать в качестве генетического маркера состояния конечностей у свиней породы ландрас. Разработанная методика тестирования позволит провести дальнейшие исследования на большем поголовье свиней различных пород и кроссов, разводимых в племенных хозяйствах РФ.
Выводы. На основе разработанной тест-системы методом пиросеквенирования были определены три генотипа ^^, AG и GG для варианта g.73467314G>A (SSC7) и установлена статистически значимая ассоциация (Р=0,003) ме^ду генотипами и состоянием задних конечностей у свиней породы ландрас. Наилучшие оценки задних конечностей имели свиньи, обладающие генотипом ^^. Отсутствие связи ме^ду генотипом ^^ и признаками откормочной и мясной продуктивности позволит проводить отбор с учетом этого генотипа, не затрагивая ростовые и мясные показатели свиней.
БИБЛИОГРAФИЯ
-
1. Genome-wide detection of genetic markers associated with growth and fatness in four pig populations using four approaches / Y. Guo, Y. Huang, L. Hou et al. // Genetics Selection Evolution. 2017. № 49. Р. 21.
-
2. Genome-wide association analyses reveal significant loci and strong candidate genes for growth and fatness traits in two pig populations / R.M. Qiao, J. Gao, Z.Y. Zhang et al. // Genet Sel Evol. 2015. № 47. Р. 17.
-
3. A genome-wide association study of social genetic effects in Landrace pigs / J.K. Hong, Y.D. Jeong, E.S. Cho et al. // Asian-Australas J Anim Sci. 2018. № 31(6). Р. 784-790.
-
4. Genome-wide association analysis reveals genomic regions on Chromosome 13 affecting litter size and candidate genes for uterine horn length in Erhualian pigs / X. Ma, P.H. Li, M.X. Zhu et al. // Animal. 2018. № 14. Р. 1-9.
-
5. Genome ‐ wide association study for reproductive traits in a Large White pig population / Y. Wang, X. Ding, Z. Tan et al. // Animal Genetics. 2018. № 49(2). Р. 127-131.
-
6. Single step genome-wide association studies based on genotyping by sequence data reveals novel loci for the litter traits of domestic pigs / P. Wu, Q. Yang, K. Wang et al. // Genomics. 2018. № 110(3). Р. 171-179.
-
7. Identification of new single nucleotide polymorphisms affecting total number born and candidate genes related to ovulation rate in Chinese Erhualian pigs / L.C. He, P.H. Li, X. Ma et al. // Animal Genetics. 2016. № 48. Р. 48-54.
-
8. Quantitative trait loci variation for growth and obesity between and within lines of pigs (Sus scrofa) / Y. Nagamine, C.S. Haley, A. Sewalem, P.M. Visscher // Genetics. 2003. № 164 (2). Р. 629-635.
-
9. A molecular genome scan analysis to identify chromosomal regions influencing geconomic traits in the pig. I. Growth and body composition / M. Malek, J.C. Dekkers, H.K. Lee et al. // Mammalian genome. 2001. № 12(8). Р. 630-636.
-
10. A genome scan reveals QTL for growth, fatness, leanness and meat quality in a Duroc-Pietrain resource population / G. Liu, D.G.J. Jennen, E. Tholen et al. // Animal genetics. 2007. № 38 (3). Р. 241-252.
-
11. Detection of quantitative trait loci for carcass composition traits in pigs / D. Milan, J.P. Bidanel, N. Iannuccelli et al. // Sel Evol. 2002. № 34(6). Р. 705-728.
-
12. Genome-wide association study for conformation traits in three Danish pig breeds / T.H. Le, O.F. Christensen, B. Nielsen, G. Sahana. Genet Sel Evol. 2017. № 49. Р. 12.
-
13. A whole genome scan for quantitative trait loci for leg weakness and its related traits in a large F2 intercross population between White Duroc and Erhualian / Y.M. Guo, H.S. Ai, J. Ren et al. // Anim Sci. 2009. № 87 (5). Р. 1569-1575.
-
14. Genome-Wide Association Study Identifies Loci for Body Composition and Structural Soundness Traits in Pigs / B. Fan, S.K. Onteru, Z.-Q. Du et al. // PLoS ONE. 2011. № 6(2). Р. e14726.
-
15. Detection of quantitative trait loci for locomotion and osteochondrosis-related traits in Large White x Meishan pigs / G.J. Lee, A.L. Archibald, G.B. Garth et al. // Anim. Sci. 2003. № 76. Р. 155-165.
-
16. Identification of genetic markers associated with fatness and leg weakness traits in the pig / B. Fan, S.K. Onteru, M.T. Nikkila et al. // Animal genetics. 2009. № 40(6). Р. 967-970.
-
17. Genome-wide association study identifies candidate genes for piglet splay leg syndrome in different populations / X. Hao, G. Plastow, C. Zhang et al. // BMC genetics. 2017. № 18(1). Р. 64.
Список литературы Эффект SNP G.73467314G>A (SSC7) на признаки продуктивности и состояние конечностей свиней
- Genome-wide detection of genetic markers associated with growth and fatness in four pig populations using four approaches / Y. Guo, Y. Huang, L. Hou et al. // Genetics Selection Evolution. 2017. № 49. Р. 21.
- Genome-wide association analyses reveal significant loci and strong candidate genes for growth and fatness traits in two pig populations / R.M. Qiao, J. Gao, Z.Y. Zhang et al. // Genet Sel Evol. 2015. № 47. Р. 17.
- A genome-wide association study of social genetic effects in Landrace pigs / J.K. Hong, Y.D. Jeong, E.S. Cho et al. // Asian-Australas J Anim Sci. 2018. № 31(6). Р. 784-790.
- Genome-wide association analysis reveals genomic regions on Chromosome 13 affecting litter size and candidate genes for uterine horn length in Erhualian pigs / X. Ma, P.H. Li, M.X. Zhu et al. // Animal. 2018. № 14. Р. 1-9.
- Genome-wide association study for reproductive traits in a Large White pig population / Y. Wang, X. Ding, Z. Tan et al. // Animal Genetics. 2018. № 49(2). Р. 127-131.


