Эффлюкс механизм и гены резистентности к тетрациклину у бактерий
Автор: Чижкова А.П.
Журнал: Форум молодых ученых @forum-nauka
Статья в выпуске: 12-4 (28), 2018 года.
Бесплатный доступ
В данной статье рассматриваются эффлюкс механизм и гены ответственные за резистентность к тетрациклину. В настоящее время идентифицировано 46 различных генов (tet) устойчивости к тетрациклину. Большинство генов (tet) кодируют один из двух механизмов резистентности к тетрациклинам: либо эффлюкс, либо рибосомную защиту.
Детерминанты устойчивости к тетрациклину, эффлюкс насосы, суперсемейство mfs
Короткий адрес: https://sciup.org/140281559
IDR: 140281559
Efflux mechanism and tetracyclin resistance genes in bacteria
This article discusses the efflux mechanism and the genes responsible for tetracycline resistance. Currently, 46 different tetracycline resistance (tet) genes have been identified. Majority genes (tet) encode one of two mechanisms of resistance to tetracyclines: either efflux or ribosomal protection.
Текст научной статьи Эффлюкс механизм и гены резистентности к тетрациклину у бактерий
В 1945 году впервые был выделен антибиотик хлортетрациклин из культуральной жидкости лучистого гриба Streptomyces aureofaciens. В 1948 году препарат начали использовать в клинической практике, а в 1952 году химическим путём, посредством восстановительного дегалоидирования хлортетрациклина, был получен полусинтетический антибиотик тетрациклин [1].
Тетрациклины проникают в бактериальные клетки путем пассивной диффузии. Тетрациклин действует путем связывания с 30S рибосомальной субъединицей, приводя к ингибированию синтеза белка. Гены, определяющие устойчивость к тетрациклину у грамотрицательных бактерий, часто обнаруживаются на транспозоне Tn10, передаваемом между ними крупными конъюгативными плазмидами [2].
Спустя год после получения тетрациклина, в 1953 году были выделены бактерии резистентные к этому антибиотику [1].
Несмотря на большую клиническую устойчивость, тетрациклины по-прежнему остаются важными препаратами для лечения различных инфекций человека, вызванных грамотрицательными и грамположительными бактериями, наряду с атипичными патогенами, включая микоплазмы, нематоды и паразитических простейших [3].
Механизм и гены антибиотикорезистентности к тетрациклину
В настоящий момент известно 46 различных генов резистентности к тетрациклину [4]. Большинство генов tet кодируют один из двух механизмов резистентности к тетрациклинам: либо отток антибиотика, либо рибосомную защиту. Рибосомная защита включает синтез белка, подобный фактору элонгации G. Он взаимодействует с рибосомой, не препятствуя синтезу белка, но и не давая тетрациклину ингибировать этот синтез [2].
Эффлюкс насосы и рибосомные защитные белки являются наиболее распространёнными типами клинической резистентности к тетрациклину и обнаруживаются у большинства патогенных бактерий человека [5].
Эффлюкс насосы являются наиболее часто встречаемы среди грамотрицательных бактерий, а рибосомные защитные механизмы устойчивости более распространены у грамположительных бактерий [6].
Эффлюкс гены грамотрицательных бактерий часто ассоциируются с конъюгативными плазмидами (гены tetA–tetE, tetG и tetH ), в то время как у грамположительных бактерий эти гены часто обнаруживают на небольших мобилизуемых плазмидах с молекулярной массой 2,7 и 2,8 МДа или хромосоме (гены tetK и tetL ). У грамположительных микроорганизмов резистентность к тетрациклину обычно ассоциируется с плазмидами [2].
Эффлюкс насосы подразделяются на 5 суперсемейств:
-
1. ABC (ATP binding cassette);
-
2. SMR (the Small Multidrug Resistance);
-
3. MFS (the Мajor Facilitator Superfamily);
-
4. RND (Resistance Nodulation Division);
-
5. MATE (the Multidrug And Toxic compound Extrusion).
Они различаются по аминокислотной последовательности, энергетическим ресурсам, затрачиваемым на экспорт антибиотика, и по субстратной специфичности [7].
К эффлюкс генам выводящим тетрациклины из бактериальных клеток относятся: otrB, otrC, tcr3, tetA, tetA(P), tetB, tetC, tetD, tetE, tetG, tetH, tetI, tetJ, tetK, tetL, tetV, tetY, tetZ, tet(30), tet(31), tet(33), tet(35), tet(38), tet(39), tet(40), tet(41), tet(42) [3, 5].
Большинство эффлюкс генов tet кодирует приблизительно 46 кДа эффлюкс белков, которые связанны с мембранной клетки [1].
Гены резистентности к тетрациклину, кодирующие эффлюкс насосы, принадлежат к суперсемейству MFS. Эффлюкс насосы разделяют на 28 классов, присутствующих в бактериях, они делятся на семь групп, которые основаны на гомологии последовательностей. Самая большая группа -первая, содержащая 12 трансмембранных спиралей. Она включает в себя следующие гены: tetA, tetB, tetC, tetD, tetE, tetG, tetH, tetZ, tetl и tet30 [3].
Все гены tet ответственные за эффлюкс, кодируют мембранноассоциированные белки, которые экспортируют тетрациклин из клетки. Выведение тетрациклина и клетки снижает внутриклеточную концентрацию препарата и, таким образом, защищает рибосомы (рис. 1)
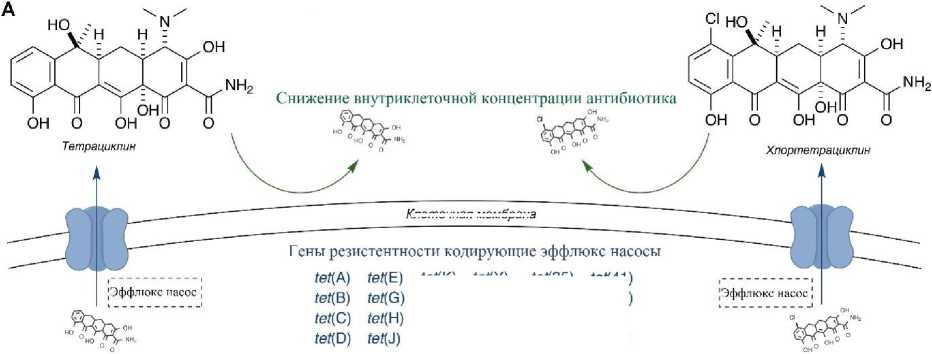
Клеточная мембрана
Рис. 1. Эффлюкс механизм резистентности к тетрациклину [5].
tef(K) fef(Y) tef(L) fef(Z) ?еИ(Р) fef(31) tef(V) te«33)
tef(35)
fef(38)
/ef(39) fef(40)
fe/(41) tef(42) tor(3) otrtC)
В 2007 году ученые изучили встречаемость генов устойчивости к тетрациклину среди кишечной палочки, выделенной от пациентов, и обнаружили, что гены tetA и tetB имели наибольшую частоту встречаемости среди изученных детерминант [8].
В 2016 году Sahar Nouri Gharajalar и Vahideh Hamidi Sofiani провели исследования по изучению распространенности детерминант устойчивости к тетрациклину у кишечной палочки, выделенных из мочи пациентов. Из 50 протестированных изолятов кишечной палочки устойчивость к тетрациклину была выявлена у 62% штаммов. ПЦР-анализ показал, что 36% изолятов содержали ген tetB и 32% бактерий содержали ген tetA. Среди всех изолятов распространенность генов tetG, tetZ, tetC, tetE, tetH и tetD составила 16%, 14%, 12%, 12%, 11% и 8% соответственно [9].
Заключение
Бактериальная резистентность к тетрациклину вследствие приобретения новых генов и / или мутации существующих уже генов увеличилась в течение последних 30 лет. Окружающая среда, несомненно, является важным резервуаром для генов устойчивости. Приобретенные бактериями гены часто связаны с мобильными элементами, которые обеспечивают распространение этих генов в различных бактериальных популяциях и экосистемах.
Если общее использование тетрациклинов, и всех антибиотиков в целом, не изменится, то это может привести к снижению эффективности современных методов лечения.
Список литературы Эффлюкс механизм и гены резистентности к тетрациклину у бактерий
- van Hoek, Angela & Mevius, Dik & Guerra, Beatriz & Mullany, Peter & Roberts, Adam & Aarts, Henk. Acquired Antibiotic Resistance Genes: An Overview // Frontiers in microbiology. - 2011. - 2. 203. URL: (Дата обращения 16.10.2018). DOI: 10.3389/fmicb.2012.00384
- Супотницкий М.В. Механизмы развития резистентности к антибиотикам у бактерий // Биопрепараты. - 2011. - № 2. - с. 4-44.
- Chopra, I. Tetracycline antibiotics: mode of action, applications, molecular biology, and epidemiology of bacterial resistance / Chopra, M. Roberts // Microbiol. Mol. Biol. Rev. - 2001. - 1. Vol. 65, -P. 232 - 260 URL: https://mmbr.asm.org/content/mmbr/65/2/232.full.pdf (Дата обращения 30.11.2018).
- M. C. Roberts and S. Schwarz. Tetracycline and phenicol resistance genes and mechanisms: Importance for agriculture, the environment, and humans // Journal of Environmental Quality. - 2016. - Vol. 45, № 2. - P. 581. URL: https://www.researchgate.net/publication/284755235 (Дата обращения 28.10.2018).
- Markley J.L., Wencewicz T.A. Tetracycline-Inactivating Enzymes // Front. Microbiol. 2018. - Vol. 9:1058. P. 1 - 27. URL: (Дата обращения 01.12.2018). DOI: 10.3389/fmicb.2018.01058
- Bryan A, Shapir N, Sadowsky MJ. Frequency and distribution of tetracycline resistance genes in genetically diverse, nonselected, and nonclinical Escherichia coli strains isolated from diverse human and animal sources // Appl Environ Microbiol. - 2004. - 70(4) P. 2503 - 2507. URL: (Дата обращения 01.12.2018). DOI: 10.1128/AEM.70.4.2503-2507.2004
- Марданова, А. М. Эффлюкс-системы SERRATIA MARCESCENS / А.М. Марданова, Л.М. Богомольная, Ю.Д. Романова, М.Р. Шарипова // Микробиология. - 2014. - Т.83. - № 1. - С.3-14.
- Tuckman M, Petersen PJ, Howe AY, Orlowski M, Mullen S, Chan K, et al. Occurrence of tetracycline resistance genes among Escherichia coli isolates from the phase 3 clinical trials for tigecycline. Antimicrob Agents Chemother. - 2007.- 51(9):3205-11. (Дата обращения 20.12.2018). DOI: 10.1128/AAC.00625-07
- Nouri Gharajalar S, Hamidi Sofiani V. Patterns of Efflux Pump Genes Among Tetracycline Resistance Uropathogenic Escherichia coli Isolates Obtained From Human Urinary Infections. Jundishapur J Microbiol. - 2017. - 10(2):e40884. - P. 1-5. URL: http://jjmicrobiol.com/en/articles/56732.html (Дата обращения 20.12.2018).


