Поиски «Ключей» доместикации животных (обзор)
Автор: Косовский Г.Ю., Глазко Т.Т.
Журнал: Сельскохозяйственная биология @agrobiology
Рубрика: Обзоры, проблемы
Статья в выпуске: 4 т.60, 2025 года.
Бесплатный доступ
Динамика глобальных экологических изменений, качественная новизна формирующихся экосистем (M.R. Kerr с соавт., 2025), сокращение биоразнообразия, в том числе сельскохозяйственных видов, привлекает все большее внимание к поискам механизмов доместикации. В этой связи рассмотрены взаимосвязи между доместикацией и ее влиянием на экологические изменения при ее проведении, основные физиологические и молекулярно-генетические системы, вовлекаемые в процессы доместикации. Накопленные данные свидетельствуют о том, что одни и те же фенотипические изменения животных в своей молекулярно-генетической основе чаще конвергентны, чем параллельны (J. Yang с соавт., 2024). При этом в изменчивость вовлекаются близкие метаболические пути, но разные гены. Отмечается, что внутри- и межвидовую дифференциацию в большей части обеспечивают метаболические пути, связанные с адаптацией к экологическим условиям, но не воздействия факторов искусственного отбора (P.A.S. Fonseca с соавт., 2024). Не выявлено качественных различий между доместицированными и близкородственными дикими видами животных по характеристикам изменчивости белок-кодирующих генов (D. Castellano с соавт., 2025) и числу их копий, превышающему известное для генов супергенных семейств между близкородственными дикими видами (X. Feng с соавт., 2017). В то же время у всех попарно сравниваемых видов животных, в том числе нетрадиционных для изучения процессов доместикаций (певчие птицы, лабораторные линии мышей, крысы, шелкопряд), наблюдаются выраженные изменения профилей генной экспрессии в структурах головного мозга. Поскольку основой формирования регуляторных систем многоклеточных организмов являются мобильные генетические элементы (транспозоны, ТЕ) и продукты их рекомбинаций, рассмотрены два основных пути вовлечения ТЕ в контроль профилей генной экспрессии: первый - сохранение генов gag экзогенных ретровирусных предшественников для формирования экзосом по типу вирусного капсида для транспорта сигнальных молекул в другие клетки (W.S. Henriques с соавт., 2024), второй - участие ТЕ в формировании сайтов связывания факторов регуляции транскрипции, интеграция ТЕ в гены, кодирующие такие факторы, а также непосредственная индукция транспозонами изменений эпигенетических характеристик разных геномных участков (метилирование ДНК, модификация гистонов, генерирование регуляторных некодирующих РНК, например кольцевой РНК, микроРНК и длинной некодирующей РНК) (A. Gebrie с соавт., 2023). Геномные сравнения домашнего, дикого кролика и реинтродуцированного в природные условия домашнего кролика свидетельствуют об ускоренном исчезновении у последнего «домашних» аллелей, в большинстве своем ассоциированных с нервной деятельностью и сайтами связывания с определенными факторами регуляции транскрипции (P. Andrade с соавт., 2024). Можно ожидать, что поиск соответствующих районов геномной ДНК будет способствовать не только уточнению механизмов доместикации, но и их практическому применению.
Доместикация, конвергентность, параллелизм, близкородственные виды, дикие виды, регуляция генной экспрессии, транспозоны
Короткий адрес: https://sciup.org/142246201
IDR: 142246201 | УДК: 636.013:575:577.218 | DOI: 10.15389/agrobiology.2025.4.604rus
Searching for “keys” to animal’s domestication (review)
The dynamics of global environmental changes, the qualitative novelty of emerging new ecosystems (M.R. Kerr et al., 2025), and the reduction of biodiversity, including agricultural species, attract increasing attention to the search for domestication mechanisms. In this regard, the relationships between domestication and its impact on environmental changes in its implementation, as well as the main physiological and molecular genetic systems involved in domestication processes are considered. Accumulated data indicate that the same phenotypic changes in animals in their molecular genetic basis are more often convergent than parallel (J. Yang et al., 2024), involving close metabolic pathways but different genes in variability. A relatively greater contribution to intra- and interspecific differentiation of metabolic pathways associated with adaptation to environmental conditions is noted compared to the action of artificial selection factors (P.A.S. Fonseca et al., 2024). No qualitative differences were found between domesticated and closely related wild animal species in characteristics of protein-coding gene variability, namely, the ratio of non-synonym-ous/synonymous substitutions in amino acid codons (D. Castellano et al., 2025), the difference in number of protein--coding gene copies exceeding those known for genes of supergene families between closely related wild species (X. Feng et al., 2017). All pairwise compared animal species, including those unconventional for studying domestication processes (e.g., songbirds, laboratory mouse lines, rats, and silkworms) show pronounced changes in gene expression profiles in brain structures. Since the formation of regulatory systems of multicellular organisms is based on mobile genetic elements (transposons, TEs) and their recombination products, two main pathways of their involvement in the control of gene expression profiles are considered: 1) preservation of gag genes of exogenous retroviral precursors to form exosomes like a viral capsid for transporting signaling molecules to other cells (W.S. Henriques et al., 2024), 2) participation of TEs in the formation of binding sites for transcription regulation factors, the integration of TEs into genes encoding such factors, and direct TE-induced changes in the epigenetic characteristics of different genomic regions, namely DNA methylation, histone modification, generation of regulatory non-coding RNAs (for example, circular RNA, microRNA and lncRNA) (A. Gebrie et al., 2023). Genomic comparisons of domestic, wild and reintroduced domestic rabbits indicate accelerated disappearance of “domestic” alleles in the latter, mostly associated with nervous activity and with binding sites for certain transcription regulation factors (P. Andrade et al., 2024). It can be expected that the search for such regions of genomic DNA will contribute not only to the clarification of domestication mechanisms, but also to their practical application.
Текст обзорной статьи Поиски «Ключей» доместикации животных (обзор)
В последние десятилетия проблемы, связанные с выявлением генетических основ доместикации, привлекают все большее внимание. Это обусловлено рядом причин — глобальным сокращением биоразнообразия, экологическими кризисами, связью между здоровьем человека и взаимодействием его как вида с окружающей средой и т.д. Особое значение приобретают сравнения доместицированных и близкородственных диких видов с целью выявления дифференцирующих их признаков и геномных элементов, что связано не только с необходимостью разработок методов ускорения селекционной работы, но и с поисками генетических детерминант фенотипического разнообразия (1). Так, доместикация была одной из основ концепции естественного и искусственного отборов Чарльза Дарвина при поисках объяснений происхождения видов и адаптаций, сформировавшей фундамент теории эволюции. Очевидно, что достижения современной молекулярной биологии приводят к необходимости пересмотра направлений поисков геномных мишеней как естественного, так и искусственного от- боров (1-3). Существенным осложнением таких поисков является отсутствие сравнительных оценок вкладов в изменчивость различных геномных элементов экологических факторов и искусственного отбора по характеристикам продуктивности.
Кроме глобальных экологических проблем и оптимизации решения селекционных задач, интерес к вопросам доместикации возрос благодаря бурному развитию молекулярной биологии, что позволило получить качественно новые данные о геномной организации и деталях работы геномов у биообъектов.
В этой связи целью настоящего обзора было сопоставление накопленных данных о связях между формообразованием и изменчивостью экологических факторов; о ресурсах геномных элементов, вовлекаемых в фенотипическую изменчивость животных, конвергентность и параллелизм в их изменчивости.
Доместикация и ее определение. Термин «доместикация» происходит от латинского слова domus — дом и подразумевает включение биообъектов в контекст экологической и социальной ниши человека, то есть того окружения и условий, в которых осуществляется взаимодействие человека со средой с целью реализации его жизненной стратегии, и организация этого контекста. Определение доместикации до сих пор остается спорным (4-13) еще и потому, что трудно отделить реакцию доместициру-емого объекта на доместикатора от влияния меняющихся задач селекционной работы (в случае человека), а также изменчивых факторов естественного отбора с учетом того, что взаимодействие доместицируемого и доместикатора неизбежно меняет и их самих, и их взаимоотношения.
Очевидно, что одомашнивание растений и животных лежит в основе формирования аграрной цивилизации. В то же время для выявления механизмов этого процесса необходимо отделять его ранние события от последующих культурных явлений земледелия и животноводства, от биологических процессов одомашнивания (4).
Доместикация является следствием выхода представителей предкового вида из его естественного экологического контекста и его интеграции в нишу человека, а также модификаций под антропогенным воздействием (5). В этой связи некоторые исследователи полагают, что процесс одомашнивания может определяться исключительно как эволюция популяций в ответ на антропогенную нишу, которые не могут существовать без нее (6, 7). В то же время другие отмечают, что большинство определений доместикации антропоцентричны и минимизируют роль бессознательного отбора и экологических факторов (8, 9), а также исключают взаимосвязь с одомашниванием других видов, разнообразие которых может обеспечить многочисленные преимущества для сельскохозяйственных систем (10).
В отношении биологических систем, вовлекавшихся в доместикацию у животных, особое внимание уделялось гипотезе о синдроме одомашнивания (наличии набора признаков доместикации у одомашненных млекопитающих), отмеченном еще Чарльзом Дарвиным (11). Некоторые из таких признаков присутствуют и у одомашненных птиц и рыб. А. Уилкинс и соавт. (11) предположили, что синдром одомашнивания обусловлен преимущественно снижением активности пролиферации и дефицитом клеток нервного гребня во время эмбрионального развития. Гипотеза привела к широкой дискуссии, продолжающейся до сих пор (12, 13), что, по-видимому, связано с многообразием организующих функций у потомков этих клеток в развитии тканей и органов многоклеточных организмов.
Деятельность человека приобрела особое значение в настоящее время, поскольку она качественно изменила многие дикие и полудикие экосистемы. Не зная механизмов их формирования, практически невозможно прогнозировать будущие состояния экосистем и разрабатывать методы их сохранения. Предполагается, что новые экологические условия создают три основных фактора — изменение климата, дефаунация и нарушение флоры, причем около 58 % плотности наземной биосферы характеризуются высокой степенью общей новизны изменений (14, 15). Эти результаты подчеркивают важность изучения реакций экосистем и биоразнообразия на растущую экологическую новизну для обоснования мер по управлению биосферой.
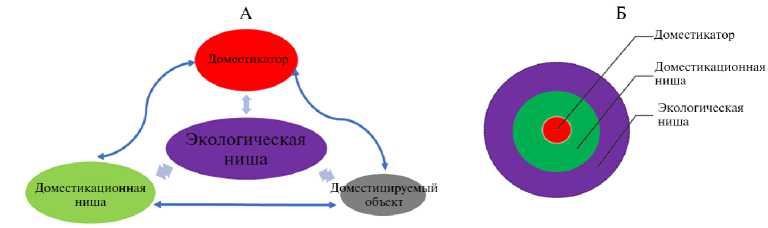
Рис. 1. Схема взаимодействий в модели доместикации (А) и встроенность подсистем модели доместикации (Б).
Условно взаимоотношения между доместикатором (человеком), объектами доместикации и биосферным контекстом (экологическими нишами) можно представить в виде вложенных друг в друга подсистем (рис. 1). При этом (см. рис. 1, Б) не рассматриваются антропогенные эффекты, существенные не только для той экологической ниши, в которой сформированы условия доместикации, но и для биосферного контекста, частью которой она является.
Конфликт между биосферой и агросферой. Конфликт и его расширение между сферой деятельности человека и его экологической нишей (16) начался задолго до формирования аграрной цивилизации (еще на этапе предшественников человека) как взаимное влияние друг на друга социальных и экологических систем. Создание специфичной для человека ниши возникло задолго до появления Homo sapiens , примерно около 3 млн лет назад (16).
К трем основным факторам, формирующим ее особенности, относят следующие (17). Первый, самый ранний — использование огня: применение последствий молний, около 1,5 млн лет назад; разработка технологий зажигания собственного огня, 200-400 тыс. лет назад; усиление их использования, когда население начало расти быстрее, 40-70 тыс. лет назад. Овладение огнем позволяло запекать и хранить клубни растений, увеличивать сохранность и использование мясных продуктов. Обогащение питания сопровождалось увеличением массы мозга по сравнению с общей массой. Вторым фактором и источником изменений стала вырубка лесов для увеличения площадей произрастания желательных растений, перемещение растений в новые условия. Третьим фактором было появление «системы орошения без сельского хозяйства» с целью увеличения числа некоторых диких растений на участках их произрастания. Самые древние каменные орудия датируются олдувайскии периодом (палеолит, олдувайская эпоха) и связаны с гомининами (группа гоминид между австралопитеками и ранними Homo ), некоторые исследователи полагают, что олдувайские орудия были изготовлены бонобо (17).
Формирование новой экологической ниши приводило к нескольким очевидным последствиям: переходу охотников-собирателей к оседлости, росту их популяционной плотности и началу доместикации растений, что приводило к их конвергентной эволюции и приобретению признаков синдрома одомашнивания (18). К таким признакам у злаков, например, относятся неосыпаемость и увеличение размеров семян, у бобовых — задержка расщепления стручков, у животных — изменения поведенческих характеристик, снижение стресс-реактивности (18, 19).
Но самые главные последствия связаны с ростом численности человека и доместицированных видов. Так, в ландшафте Земли доминируют растения, в морском ландшафте — животные. Люди и домашний скот в настоящее время вместе составляют 8 % от общей биомассы животных и примерно четверть биомассы всех наземных животных (20, 21). Анализ связей между возникновением цивилизации охотников-собирателей и сокращением мегафауны (животные массой более 10 кг) показал доминирующее значение человека в этих процессах, резко ускорившихся при постепенном переходе к аграрной цивилизации (22-24). При появлении человека его численность (как и других видов мегафауны) колебалась в пределах 100 тыс.; ее заметный рост, как предполагается, начался 70-50 тыс. лет назад, а примерно 15 тыс. лет назад (к условному началу формирования аграрной цивилизации) она могла достигать около 3-10 млн (17). К настоящему времени (12 мая 2025 года) на Земле проживает 8 221 635 063 человека (8,2216 млрд), темп прироста составляет 0,85 % в год. За последние 9 лет скорость прироста населения резко уменьшилась с 1,18 % в 2015 году до 0,85 % в 2024 .
В начале 1990-х годов широко обсуждались проблемы и возможные последствия роста народонаселения, особое внимание уделялось неравномерности такого роста в разных странах. Так, в 1994 году численность населения мира составляла 5,6 млрд человек: 1,2 млрд в промышленно развитых странах и 4,4 млрд в развивающихся (25). Разрабатывались разные программы контроля населения и планирования семьи, ожидалось, что к 2020 году численность населения мира достигнет 8 млрд человек. Шел спор о том, каков физический предел возможностей биосферы поддерживать население. Одни считали, что он достигнут уже при 5,4 млрд человек, другие — что с изменениями в потреблении и технологическом развитии Земля может прокормить 8 млрд человек. Рассматривались следующие физические ограничения: 1) конечная способность природных систем обеспечивать продовольствием и энергией, а также поглощать отходы, 2) допустимое количество парниковых газов в атмосфере без неблагоприятных побочных эффектов, 3) количество пресной воды, доступной для поддержания всех форм жизни (26). С тех пор изменилось многое (23), и обнаружилось, что проблемы с ростом народонаселения естественный отбор решает без интеллектуальной деятельности человека, объективным показателем этого служит глобальное снижение фертильности мужчин (27). Поскольку человека нередко рассматривают как «самодомести-цированный» вид (28, 29), следует напомнить, что основным препятствием для доместикации животных, по мнению J. Diamond (30), выступает повышенная стресс-реактивность. Поскольку стресс-реактивность относится к количественным признаком и зависит от ряда физиологических систем и метаболических путей (31), можно ожидать, что наблюдаемое снижение тоже является одним из показателей конфликта между биосферой и аграрной цивилизацией.
Конвергентность и параллелизм генетических основ фенотипических признаков, вовлекаемых в формирование аграрной цивилизации. Одомашнивание в некоторых случаях представляло истинную конвергенцию, при которой аналогичные состояния достигались за счет очень разных и не связанных между собой исходных молекулярно-генетических систем, и параллелизм, при котором схожие пути изменений имеют начало в схожих исходных точках, как, например, в случае таксонов с одними и теми же ортологичными генетическими локусами, ключевыми для базового онтогенеза. Некоторые черты одомашнивания, например контроль сезонности у растений, развивались параллельно у многих видов на основе одних и тех же генетических и эволюционных механизмов. Другие признаки, такие как потеря осыпаемости семян дикого типа или изменения в размере семян и плодов, достигались на основе различных генетических и онтогенетических изменений. Аналогичным образом (с точки зрения траекторий одомашнивания) ведется поиск ответов, были ли признаки доместикационного синдрома действительно параллельными у разных видов (как в случаях с пшеницей, ячменем и китайским рисом) или же они конвергировали в схожие одомашненные формы через различные метаболические пути, как выявлено у одомашненных бобовых ( Fabaceae ) и, вероятно, африканского проса (32, 33).
Доместикация животных началась позднее, чем растений, но несла в себе те же проблемы, имелось небольшое число фенотипических признаков, изменчивость которых была связана с полиморфизмом конкретных генов, оказавшихся ключевыми для отдельных признаков синдрома доместикации. Но в большинстве случаев фенотипические признаки, дифференцирующие домашние виды от близкородственных диких, были количественными и их изменчивость зависела от большого числа разных генов (34, 35). Авторы этих исследований подчеркивают, что в зависимости от генетической архитектуры признака и силы отбора как естественный, так и искусственный отбор может действовать через несколько генов с выраженными эффектами или через множество локусов с небольшим влиянием. При анализе прогресса, достигнутого за последние 35 лет в раскрытии молекулярно-генетической изменчивости, лежащей в основе фенотипического разнообразия сельскохозяйственных культур и одомашненных животных, у растений, кроме полиплоидизации, отмечается наличие многочисленных генов одомашнивания с выраженными моногенными фенотипическими эффектами, у животных — относительно б о льшая поли-генность признаков, ассоциированных с синдромом доместикации (36).
Параллелизм и конвергентность генов и метаболических путей, вовлекаемых в процессы искусственного и естественного отборов, описаны, в частности, у жвачных (37, 38). В частности, выявлены конвергентные пути и гены, участвующие в процессе репродукции у самок овец и коз, отличающие их от близкородственных диких видов, причем из 26 генов, ключевых для этих метаболических путей, только 5 являются общими для обоих видов (39).
Наглядным примером конвергентной эволюции служит изменчивость генов (синтицинов), происходящих из оболочечного гена env ретровирусов и обеспечивающих слияние клеток трофобласта при формировании плаценты. Представлены доказательства независимой кооптации этого гена у разных отрядов млекопитающих, возникновение которых разделяют миллионы лет (40). Авторы полагают, что такая конвергенция была связана с существенными преобразованиями факторов окружающей среды и вымиранием ряда видов. Проведен сравнительный анализ результатов 608
выравнивания нуклеотидных последовательностей геномов 241 плацентарного млекопитающего (41). Предполагается, что фундаментальную роль в успешных процессах видообразования и распространения плацентарных млекопитающих в палеогене выполнило сочетание двух основных событий мелового периода. Во-первых, возросшая континентальная фрагментация способствовала изоляции видов, во-вторых, быстрое появление суши во время мезозоя. Это второе событие способствовало появлению морфологически диагностируемых отрядов в экологическом вакууме, который последовал за массовым вымиранием нептичьих динозавров 66 млн лет назад (32). Процесс собственно доместикации возник уже много позднее, в период перехода от позднего плейстоцена к раннему голоцену (12000-8200 лет до н.э.) и в среднем голоцене (8200-4200 лет до н.э.) (36).
У овец и коз наблюдается конвергенция путей адаптации к одним и тем же экологическим градиентам. Так, у овец гены были в наибольшей степени связаны с адаптацией к высоте над уровнем моря, обилием и сезонностью осадков, а у коз — с летней температурой и весенними осадками. Разнообразие возможных путей адаптации — результат большого числа биологических функций, участвующих в приспособлении к многочисленным эколого-климатическим градиентам, и различной роли климатических факторов для двух видов, несмотря на их совместное распространение вдоль одних и тех же экологических градиентов (42).
Обнаруживается конвергенция фенотипических признаков, существенных при селекции, например у пород курдючных овец, несмотря на выраженные геномные различия между ними (43).
Следует отметить, что как ранние этапы доместикации, так и последующий искусственный отбор с постоянно меняющимися задачами, специфичными для разных этносов, например «липкий рис» этносов северо-восточной Азии (44) или возникновение молочного скотоводства одновременно с повышением частоты встречаемости лактазы с высокой активностью у человека в северных странах Европы (45), велся человеком на фоне экологических изменений, им же и вызываемых. В последние годы появились работы, в которых отмечается относительно более выраженный вклад в геномные адаптации к факторам естественного отбора по сравнению с искусственным. Так, более чем в 60 % производственных исследований у разных пород овец гены, участвующие исключительно в контроле признаков продуктивности, оказались вовлечены в метаболические пути, число которых в 2 раза меньше, чем число метаболических путей, связанных с адаптацией к разным экологическим условиям разведения (46). При межпородных геномных сравнениях также были более выражены ассоциации адаптаций к климату и болезням, чем к характеристикам продуктивности (47, 48). Из этого следует, что у овец экологические факторы оказывают больший эффект на межпородную дифференциацию, чем искусственный отбор.
Структурные изменения белок-кодирующих генов при доместикации. У млекопитающих сравнительный анализ влияния спонтанных мутаций по белок-кодирующим генам на приспособляемость не обнаружил выраженных различий между доместицированными и близкородственными дикими видами (34). Между представителями самой древней пары таких видов — домашней собакой и волком в белок-кодирующих генах наблюдаются существенные различия в промоторах, но не в экзонах, а также в профилях генной экспрессии в крови (49, 50).
При пангеномных исследованиях у коз (51) и овец (52) выявили высокую внутривидовую изменчивость числа белок-кодирующих генов и его относительное уменьшение у доместицированных видов по сравнению с близкородственными дикими, а также уменьшение экспрессии суперсемейств генов, связанных с обонянием у домашней свиньи по сравнению с диким кабаном (53). Однако в ряде работ у доместицированных животных описано увеличение копийности ряда генов, связанных с иммунной системой (54).
Выявленное внутри- и межвидовое разнообразие по числу копий белок-кодирующих генов в основном типично для рассмотренных в этих работах генных суперсемейств вне зависимости от доместикации. К ним, например, относятся гены иммунной системы у псовых (55), рецепторов естественных киллеров у разных видов (56), гены обонятельных рецепторов (большое семейство генов, занимающих у млекопитающих до 5 % генома, кодирующего белки), гены, связанные с поведенческими характеристиками (57, 58). Известны другие примеры повышенной изменчивости генов, связанных с прямым воздействием факторов окружающей среды (59-61). В целом, можно констатировать, что близкородственные доме-стицированные и дикие виды отличаются друг от друга по изменчивости белок-кодирующих последовательностей, особенно по генам, принадлежащим к супергенным семействам, не больше, чем дикие виды близких родов и семейств. В то же время наблюдаются различия по экспрессии ряда генов, в большинстве своем связанных с развитием и функциями нервной системы (58).
Особенности экспрессии ряда генов у доместицирован-ных и близкородственных диких видов. Изучение генной экспрессии, в частности в тканях головного мозга, на разных моделях доместикации позволило многим авторам прийти к заключению о том, что основные различия между доместицированными и дикими видами млекопитающих связаны с особенностями регуляции генной экспрессии. Так, результат сравнительного анализа распределения мононуклеотидных замен (Single Nucleotide Polymorphisms, SNP) у домашних и диких кроликов свидетельствовал о том, что наибольшее число дифференцирующих SNP локализуется в консервативных некодирующих последовательностях. Из них более 60 % SNP расположены на расстоянии 50 т.п.н. или более от ближайшего сайта начала транскрипции, то есть многие дифференцирующие SNP расположены в регуляторных элементах дальнего действия (62). Основные гены, рядом с которыми обнаруживаются дифференцирующие SNP, в большинстве своем вовлечены в функции или ранние этапы развития нервной системы (в частности, гены GRIK2 , SOX2 , KDM6B ). На этом основании был сделан вывод о том, что на начальных этапах одомашнивания животных наиболее важные фенотипические изменения связаны с поведенческими чертами адаптации животных к человеку и его нише. Они реализуются посредством изменений экспрессии генов, вовлеченных в эти процессы (62).
Например, исследованы конвергентные изменения в нейротрансмиссии в мозгу по экспрессии 488 генов рецепторов нейротрансмиттеров у 14 одомашненных видов и современного человека по сравнению с дикими и архаичными аналогами. Этот анализ выявил распространенные изменения экспрессии генов рецепторов глутамата, в первую очередь каинатных и метаботропных. Предполагается важная роль каинатных и метаботропных рецепторов в регуляции возбуждения гипоталамо—гипофизарно— надпочечниковой оси (18).
Выявлена видовая специфичность вовлечения метаболических путей в стресс-реактивность на примере генетических основ изменчивости 610
темперамента крупного рогатого скота. Описано несколько кластеров взаимосвязанных генов, изменчивость которых ассоциирована с разнообразием проявлений темперамента у крупного рогатого скота. Это кластер генов, экспрессия которых связана с ионотропной субъединицей рецептора глутамата AMPA (кодируется геном GRIA2 ); гормональный кластер генов с участием гена POMC (Proopiomelanocortin), изменчивость экспрессии которого связана с реакцией «бей или беги»; кластер генов нейронного обслуживания; кластеры генов, кодирующих белки сигнальной системы и убиквитинирования; кластер генов, участвующих в регуляции функции нейронов; кластер генов синтеза серотонина; кластер генов регуляции сплайсинга (63).
У домашних кроликов изменена архитектура мозга, что соответствует снижению эмоциональной обработки информации, в том числе внимания к поведенчески значимой стимуляции, такой как распознавание, страх, обучение, выражение эмоций и контроль, а также ухудшение обработки информации. То есть одомашнивание влияет на реорганизацию архитектуры мозга в областях и сетях, отвечающих за эмоции, когнитивные способности и поведение, что совпадает с изменением поведенческого репертуара при доместикации у многих видов млекопитающих и у птиц (64).
Европейский кролик — один из относительно недавно одомашненных млекопитающих, но он демонстрирует явные морфологические, физиологические и поведенческие отличия от своих диких сородичей. Выполнено секвенирование РНК четырех областей мозга (миндалевидное тело, гипоталамус, гиппокамп и теменная/височная кора), выделенных у новорожденных кроликов, выявлены сотни генов, дифференциально экспрессируемых у диких и домашних кроликов. Миндалевидное тело было значительно обогащено генами, связанными с дофаминергической функцией, и все 12 таких генов в этой категории показали более высокую экспрессию у домашних кроликов. В гиппокампе гены, экспрессия которых дифференцирует домашнего кролика от дикого, были в основном связанны с функцией ресничек, причем все гены в этой категории (всего 21 ген) показали снижение экспрессии у домашних кроликов. Эти результаты свидетельствуют о важных ролях дофаминовой сигнализации и функции ресничек в эволюции приручаемости во время одомашнивания кроликов (65, 66).
Высокоинбредные лабораторные линии мышей, адаптированные к человеку и лабораторным условиям, часто обозначаются как доместициро-ванные. Выполнено сравнение лабораторных линий мышей и диких предковых видов, из которых они были получены (67, 68). Выявлены 339 генов, экспрессия которых различалась у линейных мышей и представителей диких видов, в своем большинстве такая дифференцирующая экспрессия наблюдалась в тканях головного мозга.
Выполнено сравнение поведенческих характеристик линейных мышей и диких, различающихся по генотипам гена астротактина 2 (ASTN2, трансмембранный нейрональный белок, экспрессируется в мозжечке, функционирует в рецепторном трафике и модулирует синаптическую активность клеток Пуркинье). Частота референсного SNP аллеля (T) интрона astn2 составила 4,17 % у диких мышей, у двух других (C и A) — соответственно 50,0 % и 45,8 %. У классических инбредных мышей частота референсного аллеля Т (линия C57BL/6J) была равна 79,3 %, аллеля A — 20,7 %, а аллель C полностью исчез. Авторы заменили (с помощью генного редактирования) аллель Т на C и получили повышенную стресс-реактивность (67). Нокаут astn2 у линейных мышей приводит к расстройствам аутистического спектра, в частности к пониженному социальному интересу к новым объектам, заметному снижению числа ультразвуковых вокальных сигналов, вызванных разлукой, гиперактивности, повторяющемуся поведению, измененному поведению в трехкамерном тесте и нарушению мозжечково-зависимой обусловленности моргания (69).
Астротактин 2 (ASTN2) в нейрональной мембране взаимодействует с ключевым белком нейронально-глиальных адгезий и нейронной миграции ASTN1. ASTN2 непосредственно участвует в трафике рецептора адгезии ASTN1 (70). В интрон гена astn2 вложен ген trim32 , транскрибирующийся с противоположной цепи (70). Trim32 (Tripartite Motif Containing 32, или E3 Ubiquitin-Protein Ligase) участвует в нейрональной дифференцировке, его нокаут приводит к дерегуляции нескольких сотен генов, связанных с созреванием нейронов, а также с лизосомальной аутофагией (71).
Колоколизация этих двух генов эволюционно консервативна у млекопитающих и формирует пространственно связанную пару — ген astn2 , контролирующий рецепторный трафик, и ген trim32 , вовлеченный в смену программ генной экспрессии. TRIM32 входит в ось ATM—CHK2— TRIM32—ATG7. ATM — Ataxia Telangiectasia Mutated Serine/Threonine Kinase, контролер клеточного цикла, CHK2 — Checkpoint Kinase 2, контролер клеточного цикла, ATG7 — Ubiquitin-Activating Enzyme E1-Like Protein, контролирует каскад фосфорилирования-убиквитинирования, активирующий аутофагию как физиологический путь адаптации и защиты клеток, подвергшихся патологическим состояниям, которые вызваны стрессом (72).
Еще одна модель доместикации — крысы, прошедшие отбор на пониженную агрессивность. В результате выполненных исследований авторы выявили выраженную дифференциацию агрессивных и ручных крыс по экспрессии ряда генов в тканях головного мозга (73-75).
Доместикация птиц (на примере бенгальского вьюрка), как и млекопитающих сопровождалась таким же ослаблением стресс-реактивности, агрессивности, но в сочетании с повышением чувствительности к вознаграждению, а также с усложнением песен (64). Кроме того, наблюдается также определенный параллелизм изменений по smoc2 (SPARC Related Modular Calcium Binding 2, или Secreted Protein Acidic аnd Rich In Cysteine/Osteonectin/BM-40), кодирующему белок, связанный с межклеточным матриксом и адгезией клеток, мутации по которому приводят у млекопитающих к краниофациальному дисморфизму, изменениям прикуса (64). У доместицированных птиц SNP по этому гену ассоциированы с изменчивостью формы клюва (64).
Даже у насекомых, например у шелкопряда Bombyx mori , выявлены поведенческие изменения по сравнению с его диким предком Bombyx man-darina . Между ними обнаружены различия в размере мозга, также выявлены транскриптомные ландшафты, расходящиеся в процессе его развития. Показано, что в мозге домашнего шелкопряда усилена регуляция генов, связанных с иммунной системой (76). По-видимому, это прямое отражение тесных связей между нервной и иммунной системами. У млекопитающих такая связь проявляется в функциях тучных клеток — потомков нервного гребня, способных к продукции нейромедиаторов и вовлеченных в иммунные реакции и процессы воспаления (77).
С точки зрения регуляторной иерархии многоклеточного организма клетки нервного гребня (NCC) привлекают особое внимание. Уменьшение скорости их деления, по мнению некоторых исследователей, может лежать в основе синдрома доместикации, включая ювенилизацию лицевого черепа (78). Клетки нервного гребня являются транзиторными мультипотент-612
ными предшественниками, возникающими из клеток границ закрывающейся нервной трубки, затем они претерпевают эпителиально-мезенхимный переход, отслаиваются от нервной трубки и мигрируют в дорсолатеральном направлении. В зависимости от места происхождения вдоль переднезадней оси нервной трубки и постмиграционного целевого назначения NCC классифицируют как краниальные (или цефалические), сердечные, вагальные (включая энтеральные), туловищные и крестцовые. Мигрирующие NCC проходят первую точку бифуркации программ генной экспрессии (как предполагается, за счет внешнего сигнала), в которой происходит их разделение на сенсорную и нейрональную/мезенхимную линии (78).
Краниальные NCC взаимодействуют с краниальными плакодными клетками, возникающими в передней части границы нервной пластинки и образующими общую преплакодную область (78). Затем краниальные NCC, следуя миграционным потокам, формируют эктомезенхиму. В то время как активная и направленная миграция, а не пролиферация клеток стимулирует образование обонятельных, хрусталиковых и слуховых плакод, эктомезенхима расширяется за счет серии клеточных делений и только очень ограниченной индивидуальной миграцией клеток. Один клон NCC занимает определенное трехмерное пространство, называемое клональной оболочкой. Форма и размер клональных оболочек отражают локальное направленное поведение клеток (степень и полярность деления клеток), уровень смешивания с другими клонами NCC и анизотропный рост различных областей. Каждое местоположение заселено несколькими клонами, полученными из NCC, которые интенсивно смешиваются и совместно способствуют формированию различных структур.
Полярность эктомезенхимы критически важна для правильного роста элементов лицевого черепа. Нарушенное направление дочерних клеток во время деления приводит к различным патологиям, неправильно ориентированным и неправильно сформированным хондроцитам, влияющим на морфометрию лицевого черепа (78). Известные сигнальные центры, участвующие в краниофациальном морфогенезе, расположены в формирующейся нервной системе, в энтодерме передней кишки и в пространственно определенных областях лицевой эктодермы (78).
Специфическое для тканей и/или времени появление морфогенов показало, что уплотнения и, в свою очередь, хрящ, индуцируются разными сигнальными центрами в различные временные точки как независимо формируемые структурные единицы, что указывает на составной характер хондрокрания и будущего черепа. Фронтоназальная эктодермальная зона птиц и млекопитающих представляет сигнальный центр в лобной эктодерме лицевого черепа (78).
NCC дают начало широкому спектру типов клеток, таких как нейроны и глиальные клетки периферической нервной системы, в частности, эндокринные клетки, меланоциты, тучные клетки. Их специализация зависит от межклеточных контактов и дистантных регуляторных сигналов. У бета-клеток поджелудочной железы, меланоцитов, тучных клеток ключевым белком их регуляторной функции по отношению к другим тканям и органам служит меланофилин — транспортер экзосом, необходимых для адресной передачи молекулярных регуляторных сигналов (78).
Анализ динамики клеточных популяций NCC свидетельствует о том, что именно они выполняют ведущую роль в организации иерархии органов и тканей на ранних этапах развития. По-видимому, это и послужило основой для формирования представлений о ключевой роли NCC в основах синдрома доместикации (11).
Вовлечение транспозонов в регуляторные процессы. Накопленные данные о преимущественном вовлечении в дифференциацию между доместицированными и дикими близкородственными видами некодирующих белки последовательностей позволяют выделить приоритетную область поиска ключевых генетических элементов, изменчивость которых лежит в основе доместикации и ответов на факторы искусственного и естественного отборов. Это регуляция генной экспрессии и контроля смены ее программ. Ведущую роль в появлении и изменчивости геномных элементов контроля генной экспрессии выполняют мобильные генетические элементы, или транспозоны (ТЕ), а также их производные (1, 2, 79).
Транспозоны (ТЕ) представлены двумя классами: I — ретротранспозоны (потомки экзогенных ретровирусов), II — DNA-транспозоны (потомки экзогенных ДНК-содержащих вирусов). Ретротранспозоны подразделяются на автономные (несущие ген обратной транскриптазы pol , обеспечивающий синтез провирусной ДНК, котрая встраивается в геном хозяина) и неавтономные (без pol) (80). Автономные ретротранспозоны подразделяются на несущие длинные концевые повторы (Long Terminal Repeat, LTR), получившие название эндогенных ретровирусов (ERV, несут три основных гена — gag, pol, env ), и не несущие LTR длинные диспергированные ядерные элементы (Long Interspersed Nuclear Element, LINE). Неавтономные ретротранспозоны называют короткими диспергированными ядерными элементами (Short Interspersed Nuclear Element, SINE), в основном это потомки генов, кодирующих РНК, которые обслуживают процессы трансляции у эукариот (80). Примеры — РНК 7SL, участвующая в транспорте и прикреплении мРНК экспортируемых в межклеточное пространство белков к канальцам эндоплазматического ретикулюма, транспортная РНК, рибосомальная 5S-РНК (последняя в основном у растений) (80). Распространение SINE возможно только с участием обратной транскриптазы LINE (80). У человека еще выделяют сложный SINE — элемент SVA, состоящий из области, связанной с Alu (7SL), области тандемных повторов с переменным числом оснований (VNTR) и последовательности SINE-R, гомологичной фрагменту эндогенного ретровируса человека HERV-K10 (80). ДНК-транспозоны в основном представлены потомками эндогенных ДНК-вирусов hAT, Tc/Mariner, Helitron (80).
Участие транспозонов в формировании биоразнообразия начиналось достаточно давно. Сама многоклеточность возникла почти полмиллиарда лет назад, ей предшествовало увеличение выживания прокариот за счет включения в собственный геном чужеродной ДНК для защиты от ее же действия (предшественник системы CRISPR/Cas9), затем происходило увеличение популяционно-генетического разнообразия за счет экзаптации (кооптирования) чужих генов, приобретающих новые биологические функции, то есть одновременно формировались и защита, и более высокая приспособленность (81). Некоторые исследователи полагают (82), что примерно в это же время (между 460 и 550 млн лет назад), когда возникала мно-гоклеточность, начали эволюционировать мобильные генетические элементы, необходимые для межклеточных взаимодействий. В одних случаях при таких взаимодействиях обеспечивалась прямая передача сигнальных молекул, в других — происходила индукция смены программ генной экспрессии в разных клеточных популяциях, принимающих эти сигналы с участием биомолекул-посредников (82).
Кооптирование генов в сигнальные системы многоклеточного организма. Одомашнивание генов ретровирусов у млекопитающих включает два 614
правила (на примере генов env , необходимых для слияния плазматических мембран клеток хозяина и уклонения от иммунитета). Во-первых, один и тот же вирусный белок может быть независимо перепрофилирован для аналогичных функций у разных хозяев (примеры — семь разных путей формирования клеток трофобласта у млекопитающих, и другой путь у некоторых ящериц). Во-вторых, одомашненные копии одного вирусного домена могут выполнять различные функции даже у одного и того же хозяина (например, защита от ретровирусов у кур, мышей, кошек, овец и человека) (83, 84).
Гены gag кодируют полипротеин, включающий домены капсида (CA), матрикса (MA) и нуклеокапсида (NC), которые вместе упаковывают вирусный геном во время сборки вириона. Одомашненные гены CA собираются в структуры, подобные капсиду, выполняют важные функции в осуществлении воспроизводства хозяина и нейронной активности (84). Один из потомков gag ген arc (Activity-Regulated Cytoskeletal-associated) у позвоночных, произошедший от древнего ретроэлемента из клады Metaviridae (ранее известной как Ty3/Gypsy). Белок ARC образует структуры, подобные капсидам CA gag , и функционирует в мозге в качестве сигнального узла и РНК-переносчика в нейронах, регулируя обучение и память. Независимое событие одомашнивания от отдельной линии Metaviridae привело к появлению гена darc1 у видов Drosophila , который также кодирует структуры, подобные домену капсида CA, и упаковывает мРНК для межклеточной нейронной сигнализации (84).
Как независимые древние события одомашнивания представителей Metaviridae , так и дупликации после одомашнивания привели к появлению более двух десятков одомашненных gag -подобных генов в геноме человека, включая arc и два небольших семейства генов, часто именуемых семействами PNMA (паранеопластические Ma-антигены) и SIRH/RTL (связаны с Sushi-Ichi ретротранспозон-гомологи/ретротранспозон-подобные) (84). В геноме человека выявлено более 200 ортологов, подобных генам, кодирующим капсидный домен СА. Их выравнивание позволило прийти к выводу о независимой множественной геномной интеграции ретровирусов, формирующих кластеры последовательностей капсидных доменов СА. Описаны по крайней мере четыре независимых события одомашнивания метавирусов, у потомков которых выявлены структурно различные N-концевые домены СА (85).
У тетрапод представлена филогения на основании аминокислотных последовательностей продуктов генов gag (имеют гомологию с генами arc ), pol , env и нуклеотидных последовательностей длинных концевых повторов (LTR) из родственных ретротранспозонов Ty3/Gypsy. Полученные результаты свидетельствовали о независимых событиях кооптации гена arc (86). Белок ARC млекопитающих демонстрирует характерные черты белков GAG, кодируемых ретровирусами и ретротранспозонами (самосборка в капсиды, инкапсуляция РНК, высвобождение и межклеточная передача РНК). ARC опосредует межклеточный трафик мРНК через внеклеточные везикулы, раскрывая новый молекулярный механизм, посредством которого генетическая информация передается между нейронами (86).
Ретровирусная инкапсуляция вирусной геномной РНК представляет собой cложный процесс, опосредованный сетью взаимодействий между GAG, РНК и липидными мембранами. GAG вируса иммунодефицита человека содержит цинковые пальцы в лидирующем NC-домене, которые опосредуют связывание и отбор вирусной РНК, но в отсутствие вирусной РНК GAG также может связывать клеточные мРНК. GAG флоами вируса не содержат цинковых доменов и связывают РНК через С-концевые участки, богатые глицином и аргинином, что указывает на наличие у ряда семейств вирусов различных GAG-доменов, выполняющих сходные биохимические функции. ARC млекопитающих не содержит цинковых доменов, но может связывать РНК посредством ионных взаимодействий с N-концом. Капсиды prARC проявляют низкую специфичность к конкретной мРНК, но инкапсулируют большое количество РНК в соответствии со стехиометрией, защищая РНК от деградации РНКазой (86).
В нейронах кооптированные гены ретротранспозонов выполняют двойную функцию, участвуя в контроле памяти и индукции иммунной реакции. Так, они обеспечивают регулируемую белками GAG передачу РНК от пресинаптического нейрона к постсинаптическому, которая модулируется экспрессией эндогенных ретроэлементов с образованием двуцепочечных РНК, индуцирующих интерферон. Он способствует локальному ремоделированию дендритов и разрушению синаптических контактов. Эти изменения защищают от нежелательной передачи РНК, но ухудшают формирование памяти (87). В геноме человека описаны 24 гена, близкие по нуклеотидным последовательностям и по функциям к генам gag , в частности гены pnmal (Neuron- and Testis-Specific Protein 1) и pnma4 (Proteasome 20S Subunit Alpha 4, кодирует субъединицу протеазы, разрушающую белки по убиквитиновому типу) (88).
Еще одним примером кооптирования генов ретровирусов служит возникновение семейства генов bex , в частности кодирующих рецептор фактора роста нейронов ( bex 3 , Brain Expressed X-Linked 3), посредством внедрения в последовательности предшественников плацентарных ретротранспозонов (HAL1b, L1ME-like) (89).
В целом имеющиеся данные показывают, что кооптированные гены ретровирусов активно участвуют в обмене регуляторной информацией между клетками по механизму формирования капсидов у экзогенных ретровирусов. После образования и высвобождения внеклеточных везикул, несущих мРНК или некодирующие регуляторные РНК и ассоциированные с ними белки, происходит передача везикул в клетки-реципиенты. Это приводит к модификации хроматина и факторов регуляции транскрипции, существенно меняя эпигеном клеток как в норме, так и при патологиях (90-92).
Включение нуклеотидных последовательностей транспозонов в регуляторные сети, контролирующие профили генной экспрессии. У всех многоклеточных ТЕ присутствуют и высокоизменчивы, что особенно наглядно выявляется при пангеномном анализе в самых малых геномах у беспозвоночных (дрозофила), однодольных растений (рис), позвоночных (рыбка Данио) (93). ТЕ существенно варьируют от таксона к таксону, в частности от вида к виду, в том числе у доместицированных видов животных (94). Например, домашний кролик отличается от других млекопитающих тем, что у него среди ТЕ доминирует SINE (тРНК), тогда как у большинства других видов — LINE (95).
Мобилом домашнего кролика содержит четыре семейства и 19 подсемейств LINE1, два семейства и девять подсемейств SINE и 12 семейств ERV (95). Ряд семейств и подсемейств эволюционно очень молоды и могут оставаться активными, например L1B, L1D, OcuSINEA и OcuERV1. Ландшафт мобильных элементов в геноме включает около 2 млн копий SINE, представляющих наибольшую долю генома (19,61 %), за которыми следуют LINE (15,44 %) и LTR (4,11 %), что значительно отличается от состава большинства мобиломов других млекопитающих. Выявлена очень 616
высокая частота полиморфизмов вставок (> 85 %) для самого молодого подсемейства (OcuSINEA1). Большинство вставок ретротранспозонов перекрывались с белок-кодирующими областями (> 80 %) и генами длинных некодирующих РНК (Long Noncoding RNA, lncRNA) (90 %) (95).
Среди SINE домашнего кролика обнаружены два необычных семейства — OcuSINEA и OcuSINEB, которые имеют происхождение, не связанное с тРНК, но несут выраженную гомологию с соответствующими LINE. Это позволяет допустить, что эти SINE домашнего кролика кооптировали гены эндонуклеаз LINE. Кроме того, эволюционный анализ динамики вставок и утрат ERV выявил особенности, характерные для домашнего кролика (95). Так, 100-80 млн лет назад в геноме кролика произошел всплеск размножения общих для млекопитающих ERV (ERVL, сохраняет у некоторых видов транспозиционную активность, ERVL-MaLR, ERV класса 1 и ERV класса III), а затем они были почти полностью вытеснены семействами OcuERV1 и OcuERV2, принадлежащими к группе гамма-ERV (95) .
Тем не менее следует отметить, что все ТЕ потенциально могут индуцировать эпигенетические изменения — метилирование ДНК, модификацию гистонов, а также генерировать образование регуляторных некодирующих РНК (например, кольцевой РНК, микроРНК и длинной некодирующей РНК, соответственно circle RNA, microRNA и lncRNA) (96). Независимо от происхождения, они непосредственно включены в регуляторный оборот факторов регуляции транскрипции (TF) в связи с особенностями взаимоотношений с регуляторной системой хозяина (ТЕ изначально несут сайты связывания с TF; сами TF возникают с участием ТЕ) (97). В общем, все ТЕ, даже принадлежащие к разным классам, имеют общие черты, связанные с механизмами их репликации, транспозиции, интеграции, взаимодействий с генами хозяина (как на уровне ближайших соседей, так и на разной удаленности), а также вовлеченности в 3D организацию генома (97).
Сложность анализа вовлечения ТЕ и их продуктов в регуляторные сети прежде всего заключается в высокой скорости рекомбинаций между ними (пример — сетевые рекомбинации между доменами LINE) (98). Один из результатов рекомбинаций между ТЕ — появление длинной некодирующей РНК (lncRNA). lncRNA признаны ключевыми игроками в регуляции активности генов, влияющими на организацию и экспрессию генома посредством либо нековалентного взаимодействия с ДНК-связан-ными белками, либо прямого специфичного для последовательности взаимодействия с образованием триплексов РНК:ДНК (99). Число аннотированных lncRNA, тесно связанных с ТЕ, неуклонно растет и в настоящее время превысило 20000. Достаточно часто в 5´-конце lncRNA присутствует последовательность LTR ERV, которая содержит большое число регуляторных мотивов и может создавать условия для транскрипции соответствующей геномной области (99).
Описаны примеры участия lncRNA в удлинении, процессинге или сплайсинге, инициации или активации транскрипции соседнего гена, в формировании каркаса для посадки регуляторных белков, стабилизации транскрипции или ее угнетения, модуляции эффектов факторов регуляции транскрипции, ядерной компартментализации регуляторных факторов, опосредованной взаимодействиями между длинными некодирующими РНК и белками-регуляторами (100).
Известно, что в геномах с достаточно большой частотой встречаются LTR без собственно «тела» ERV (такие последовательности получили название LTR solo) (101). Но они содержат большое количество регуляторных мотивов, в том числе сайт инициации транскрипции. В этой связи последовательность, идущая за ним, может транскрибироваться, рекомбинировать с другими ТЕ и приобретать новые свойства. Анализ, выполненный на геномах овец и коз, показал широкую представленность lncRNA и в белок-кодирующих генах, и в разных ERV (101).
Наглядным примером высокой плотности распределения регуляторных элементов в длинных концевых повторах (LTR) может быть экзогенный ретровирус бычьего лейкоза BLV (102) (рис. 2).

Рис. 2. Схема последовательности LTR ретровируса бычьего лейкоза BLV (102).
Область U3 содержит канонический промотор CAT-бокс (CCAACT в координатах от - 97 до - 92) и TATA-боксы (GATAAAT между позициями - 44 и - 38). В LTR ключевой регуляторный элемент содержит тройную копию из 21 нуклеотида (TRE1, TRE2, TRE3, см. рис. 2). Они являются якорными последовательностями, содержащими элементы, регулируемые циклической AMP (cyclic-AMP Responsive Element, CRE). Последовательность из 21 нуклеотида является также мишенью связывания с белком Tax — активатором транскрипции вируса. Внутренние CRE-подобные последовательности (GACGTCA, TGACG, TGAC, TCA) близки к консенсусу CRE TGACGTCA. Еще один регуляторный мотив в 21-нуклеотидной последовательности, локализованный близко к ее 5´-концу, необходим для ответа на глюкокортикоиды. Дополнительно регуляторные элементы локализованы в последовательности R. В области U5 находятся участки связывания с IRF-1 и IRF-2 (Interferon Regulatory Factor 1 и 2), которые стимулируют базовую экспрессию в отсутствие Tax. LTR также несет потенциально регуляторные мотивы (инвертированные повторы, G4 квадруплексы, триплексы) (102).
Таким образом, по крайней мере в тканях головного мозга ТЕ сохранили способность создавать транспортные везикулы (по типу капсидов вирусов), переносящие информационные молекулы от одной клетки к другой (без чего невозможно представить многоклеточные сообщества) и создали динамичную, обновляющуюся сеть регуляторных элементов, контролирующих профили генной экспрессии.
Отбор против аллелей доместикации на примере реинтродукции домашнего кролика в природные условия. Выполнен полногеномный сравнительный анализ интродуцированных популяций кроликов, отобранных в нескольких местах на трех разных континентах, что соответствует шести событиям колонизации (два в Южной Америке, по одному в Австралии, Новой Зеландии, Англии, Швеции). Для сравнения дикие кролики были отловлены в нескольких местностях их родного ареала (Иберия и Франция) и семь домашних пород (103). Обнаружено, что у интродуцированных кроликов во всех группах наблюдается общегеномная характеристика — более выраженный отбор против аллелей, частота которых сильнее увеличилась во время одомашнивания. Эта закономерность была сильнее вблизи генов с функциями, связанными с работой головного мозга, что может быть важно для компенсации сниженной реакции страха и бегства, характерной для домашних кроликов. В остальном мишени отбора при интродукции не были общими для разных популяций. Более того, при реинтродукции аллели окраса шерсти оказались мишенью естественного отбора, но его интенсивность была неодинакова для разных фенотипов. В частности, наименее выраженно отбор влиял на частоту встречаемости кроликов с разбавленным серым окрасом (103).
Выполнен сравнительный анализ по SNP французской (wildFR), венгерской (wildHU) и иберийской (wildIB) популяций дикого кролика (104). В результате обнаружена их четкая дифференциация от пород домашнего кролика. Причем две японские породы сгруппировались ближе друг к другу, остальные подразделились на небольшие группы, в целом близкие по происхождению и направлениям продуктивности: новозеландские белые, калифорнийские, хайкольские и кролики Зика (мясные); кролики Рекс и ангорские (шерстные); тюрингенские, нидерландские карликовые и голландские (породы с небольшим телом) (104). На основании плотности распределения SNP, дифференцирующих диких и домашних кроликов, отобраны хромосомные регионы, которые могут быть мишенями отбора (104). Как у домашних, так и у диких животных идентифицированы многочисленные варианты таких регионов, два из которых, как было обнаружено, фиксированы на разных аллелях в двух популяциях. Некоторые из предполагаемых мишеней отбора не перекрывались ни с одним известным геном в геноме кролика, что указывает на важность этих межгенных участков. Обогащение выбранных регионов сайтами связывания с определенными факторами транскрипции предполагает возможную роль и выявленных хромосомных регионов, и соответствующих регуляторных элементов в процессе доместикации.
Итак, современные данные свидетельствуют о том, что исторически в формообразовании млекопитающих активное участие принимали факторы окружающей среды, такие как изоляция животных и освобождение ниш. Периоды, предшествующие доместикации, сопровождались последовательным расширением и усилением влияния на окружающую среду новой ниши, формируемой человеком, что, в свою очередь, приводило к вытеснению видовых сообществ. В настояшее время это привело к доминированию среди наземных млекопитающих человека и доместицирован-ных видов животных. Известное сокращение биоразнообразия не обошло и человека, скорость роста численности которого уменьшилась. Сравнение близкородственных доместицированных и диких видов животных позволило прийти к выводу о том, что на геномном уровне наблюдаются конвергентные и параллельные изменения, причем в конвергентные вовлекаются близкие метаболические пути, но разные гены. Выявлено относительно большее влияние адаптации к экологическим условиям при доместикации по сравнению с ответом на искусственный отбор. Отмечается отсутствие выраженных различий по белок-кодирующим последовательностям и их копийности между близкородственными доместицированными и дикими видами животных, однако такие различия обнаруживаются в экспрессии генов. Наибольшие различия по экспрессии наблюдаются в генах, ассоциированных с иммунной системой, нервной деятельностью и характеристиками воспроизводства. Действие регуляторных сетей генной экспрессии, формируемых транспозонами и их производными, в основном заключается в участии в трафике сигнальных молекул между клетками и адресном влиянии на эпигеномное состояние разных участков генома. Полученные данные по сравнительному геномному анализу домашнего, дикого и реинтродуцированного в природные условия домашнего кролика свидетельствуют об ускоренном исчезновении у последнего «домаш- них» аллелей в большинстве своем связанных с нервной деятельностью и с сайтами взаимодействия с факторами регуляции транскрипции. Учитывая тесные связи между функциями нервной и иммунной систем, можно ожидать, что контроль таких сайтов будет способствовать выявлению «ключей» не только доместикации, но и адаптации к меняющимся условиям окружающей среды.


