Программа определения и анализа ассоциациированности видов в экологических сообществах
Автор: Селезнев Д.Г.
Журнал: Самарская Лука: проблемы региональной и глобальной экологии @ssc-sl
Рубрика: Краткие сообщения
Статья в выпуске: 3 т.32, 2023 года.
Бесплатный доступ
Описана разработанная автором методика выделения ассоциаций видов, которая отличается простотой реализации, устойчивостью и воспроизводимостью результатов. Недостатком методики является использование только качественных данных о наличии или отсутствии вида в пробе, а не его количественных характеристик.
Видовые ассоциации, статистическая методика, общая сила связности
Короткий адрес: https://sciup.org/148327557
IDR: 148327557 | УДК: 574.9 | DOI: 10.24412/2073-1035-2023-10498
Definition and analysis program associations species in ecological communities
The method developed by the author for identifying species associations is described, which is characterized by ease of implementation, stability and reproducibility of results. The disadvantage of the technique is the use of only qualitative data on the presence or absence of a species in a sample, and not its quantitative characteristics.
Текст краткого сообщения Программа определения и анализа ассоциациированности видов в экологических сообществах
Важной 1 частью анализа качественных экологических данных является выявление видовых ассоциаций, обусловленных прямыми (трофические, топические, фориче-ские и др.) и косвенными (общность биото-пических условий, характер питания, защита от хищников) межвидовыми отношениями (Odum, Barrett, 1971). С этой целью было разработано несколько специализированных матричных индексов, для определения уровня значимости которых предлагается использовать одну из девяти рандо-мизационных процедур построения теоретического распределения индекса (Gotelli, 2000). Однако в экологических исследованиях задача определения видовых ассоциаций решается сравнительно редко из-за неочевидности математического аппарата и сложности его реализации.
Автором была разработана статистическая методика выделения положительных и отрицательных ассоциаций видов, позволяющая избежать использования матричных индексов и рандомизационной процедуры определения их уровня значимости. Для этого на бинарной матрице встречаемости видов в экологических пробах ис- пользуются дискретные гипергеометрическое или биномиальное распределения, дающие оценку вероятности наблюдаемой совместной встречаемости пар видов. Критическая область функции распределения (confidence intervals of distribution) позволяет принять одно из трех решений: пара видов отрицательно либо положительно ассоциирована или их совместная встречаемость в пробах носит случайный характер. В качестве альтернативы критической области возможно использование байесовского вывода (Bayesian inference), где в качестве оцениваемого параметра может быть взята любая равномерно распределенная наблюдаемая характеристика, например, общее число проб, а в качестве генеративной функции – функция вероятности дискретного распределения.
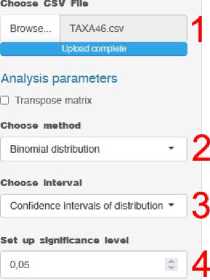
Предложенная методика реализована в виде web-приложения, размещенного на сервере Института биологии внутренних вод по адресу (рис. 1). Приложение написано на языке R в среде Shiny (Chang et al., 2023) и позволяет проанализировать бинарную пользовательскую матрицу формата «виды – пробы» с использованием двух дискретных распределений с заданной критической областью или с помощью байесовских доверительных интервалов (credible intervals of Bayesian inference). Исходная матрица может быть транспонирована для определения ассоциаций между пробами по видовому со- ставу или, другими словами, определения фаунистического сходства. Полученные результаты в виде списка ассоциированных видов или проб могут быть сохранены в формате CSV для дальнейшего анализа.
Species association analysis
® All 301 pairs
О 248 positively associated pairs
О 53 negatively associated pairs
Calculate
Method
i Download

Result
Graph Graph analysis
Search:

Graph parameters
S Species names abbreviations
Nodes position method
Kamada-Kawai (fixed)
Nodes clustering method
Multi-level optimization of modularity

Draw and analyze graph
entries
Рис. 1. Интерфейс web-приложения Species association analysis. Цифрами обозначены: 1 – загрузка пользовательского файла, 2 – выбор статистического распределения, 3 – выбор метода определения видовых ассоциаций, 4 – пороговый уровень значимости, 5 – выбор алгоритма расположения (layout) узлов графа, 6 – выбор алгоритма кластеризации узлов графа Fig. 1. Interface of the Species association analysis web application. The numbers indicate: 1 – loading a user file, 2 – choosing a statistical distribution, 3 – choosing a method for determining species associations, 4 – threshold level of significance, 5 – choosing an algorithm for the layout of graph nodes, 6 – choosing an algorithm for clustering graph nodes
Для визуализации результатов анализа с помощью пакета igraph (Csardi, Nepusz, 2006) приложение строит неориен-тируемый граф, где в качестве узлов представлены виды из списка ассоциированных, а в качестве ребер – выявленные ассоциации между ними. Размер маркера узла пропорционален частоте встречаемости вида, а толщина ребра пропорциональна силе свя- зи через настраиваемые коэффициенты (рис. 2).
Взаимное расположение узлов на графе может быть определено с помощью трех алгоритмов (выпадающий список 5 на рис. 1), одним из которых является метод многомерного шкалирования (MDS). Этот метод часто строит не оптимальный с визуальной точки зрения граф, но расположе- ние вершин в нем несет дополнительную информацию о представленных фаунистических комплексах. На рис. 2 в кластер I входят реофильные пресноводные виды, в кластер II – лимнофильные пресноводные, в кластер III – лимнофильные эвригалин-
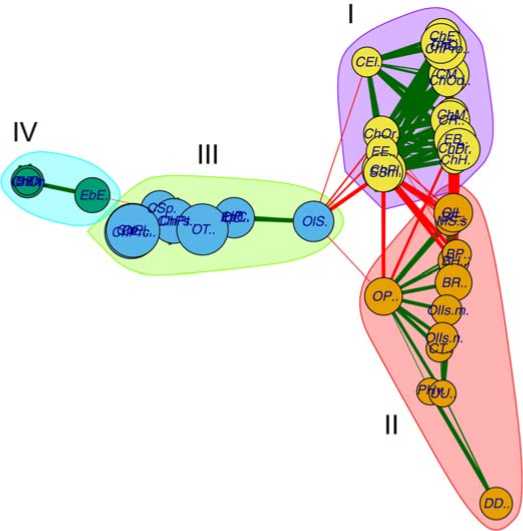
Рис. 2. Граф положительно ассоциированных видов макрозообентоса средних и малых рек бассейна Нижней Волги (Golovatyuk et al., in press). Выделение ассоциаций: биномиальное распределение с 5% верхней критической областью. Расположение вершин методом MDS Fig. 2. Graph of positively associated macrozoobenthos species of medium and small rivers of the Lower Volga basin [Golovatyuk et al. In press]. Identification of associations: binomial distribution with 5% upper critical region. Location of vertices using MDS method
ные, в кластер IV – лимнофильные гало- фильные виды. Таким образом, на графе по оси абсцисс расположен градиент солености воды, а по оси ординат – градиент скорости течения.
Группировка узлов в кластеры также осуществляется с помощью различных алгоритмов, использующих принцип максимизации модулярности графа (выпадающий список 6 на рис. 1). Отдельно можно выделить алгоритм Optimal community structure, добивающийся максимально возможной модулярности средствами целочисленного программирования, но имеющий экспоненциальную сложность (Brandes et al., 2008). Если в визуализацию включены отрицательно ассоциированные виды, задачей алгоритма кластеризации является максимизация отрицательных и минимизация положительных связей между кластерами. Эту задачу успешно решает доработанный алгоритм Affiinity propagation, корректно обрабатывающий отрицательные веса ребер (Traag, Bruggeman, 2008), тогда как остальные алгоритмы считают их нулевыми.
В приведенном рис. 2 кластеризация по- ложительно ассоциированных видов осуществлялась методом многоуровневой оптимизации модулярности (Muli-level optimization of modularity) (Blondel et al., 2008). Кроме указанных выше солености и скорости течения, распределенных по ортогональным осям графа, алгоритм кластеризации учел температуру воды и тип грунта, не имея о них явных данных. Так от кластера I к кластеру IV температура воды в летний период последовательно повышается с 16,9 °C до 27°C, а грунт меняется от гравийно-галечного через заиленный песок и глину до черного ила в кластере IV.
В web-приложении на вкладке «Graph analysis» выделенные кластеры анализируются по плотности связей и их средней силе в кластере. Интегральная характеристика, названная «общей силой связности» (total connectivity strength) объединяет относительное число и среднюю силу связей в кластере в единую нормированную характеристику, позволяющую сравнивать кластеры между собой.
Предложенная методика отличается простотой реализации (для проверки степени ассоциированности видов возможно использование MS Excel 2010+), а также устойчивостью и воспроизводимостью ре
СПИСОК
Список литературы Программа определения и анализа ассоциациированности видов в экологических сообществах
- Blondel V.D., Guillaume J.-L., Lambiotte R., Lefebvre E. Fast unfolding of communities in large networks // Journal of Statistical Mechanics: Theory and Experiment. 2008. P10008. P. 1-12. DOI: 10.1088/1742-5468/2008/10/P10008
- Brandes U., Delling D., Gaertler M., Gorke R., Hoefer M., Nikoloski Z., Wagner D. On Modularity Clustering // IEEE Transactions on Knowledge and Data Engineering. 2008. Vol. 20, iss. 2. P. 172-188. DOI: 10.1109/TKDE.2007.190689
- Chang W., Cheng J., Allaire J., Sievert C., Schloerke B., Xie Y., Allen J., McPherson J., Dipert A., Borges B. shiny: Web Application Framework for R. R package version 1.7.4.1. 2023. [https://CRAN.R-project.org/package=shiny].
- Csardi G., Nepusz T. The igraph software package for complex network research // International journal of complex systems. 2006. Vol. 1695 (5). P. 1-9. [https://igraph.org].
- Golovatyuk L.V., Seleznev D.G., Kurina E.M. Analysis of macrozoobenthos species associations in the eastern european plain under conditions of changing climatic zones // Hydrobiologia. (In press).
- Gotell N.J. Null model analysis of species co-occurrence patterns // Ecology. 2000. Vol. 81, iss. 9. P. 2606-2621. [2606:NMAOSC]2.0.CO;2. DOI: 10.1890/0012-9658(2000)081
- Odum E.P., Barrett G.W. Fundamentals of Ecology. Third edition. Philadelphia: Saunders, 1971. 574 p.
- Traag V.A., Bruggeman J.Community detection in networks with positive and negative links //Physical Review E. 2008. Vol. 80, iss. 3. P036115. DOI: 10.1103/PhysRevE.80.036115


