Разработка методики молекулярно-генетической паспортизации штаммов сельскохозяйственных микроорганизмов с помощью AFLP-фингерпринтинга
Автор: Сафронова В.И., Чижевская Е.П., Андронов Е.Е.
Журнал: Сельскохозяйственная биология @agrobiology
Рубрика: Санитария, экология, микробиология
Статья в выпуске: 6 т.47, 2012 года.
Бесплатный доступ
Объектом исследования были 16 штаммов из Ведомственной коллекции полезных микроорганизмов сельскохозяйственного назначения Россельхозакадемии (ВКСМ), относящиеся к родам Bacillus, Lactobacillus, Rhizobium и Bradyrhizobium. Целью работы была разработка методики генотипической паспортизации штаммов с помощью AFLP-фингерпринтинга, обеспечивающего детекцию нуклеотидного полиморфизма и мелких геномных перестроек. В результате исследований разработан протокол проведения AFLP-фингерпринтинга, начиная от выделения ДНК из клеток микроорганизмов и заканчивая компьютерной обработкой данных. Показано, что метод AFLP-фингерпринтинга обладает высокой штаммовой специфичностью, разрешающей способностью и воспроизводимостью результатов. Метод может быть использован для получения индивидуальных генетических паспортов микроорганизмов, депонируемых в ВКСМ, в целях защиты авторских прав на коммерческие штаммы.
Микробиологическая коллекция, генетическая паспортизация коммерческих штаммов микроорганизмов, aflp-фингерпринтинг
Короткий адрес: https://sciup.org/142133353
IDR: 142133353 | УДК: 631/635:579.64:57.088
Optimization of the AFLP-fingerprinting method for a molecular-genetic certification of agricultural microorganisms
The study involved 16 strains of the Russian collection of agricultural microorganisms (RCAM) related to the genera Bacillus, Lactobacillus, Rhizobium, and Bradyrhizobium. The aim of the work was to develop a procedure of the genotypic certification of strains with AFLP-fingerprinting (amplified fragment length polymorphism), providing detection of nucleotide polymorphisms and small rearrangements. As a result the protocol of AFLP-fingerprinting, ranging from the isolation of DNA from microbial cells and ending with computer data processing is developed. It is shown that the method of AFLP-fingerprinting has a high specificity, resolution and reproducibility of results. This method can be used to obtain individual genetic passports of microorganisms deposited in the RCAM, in order to protect the copyright of the commercial strains.
Текст научной статьи Разработка методики молекулярно-генетической паспортизации штаммов сельскохозяйственных микроорганизмов с помощью AFLP-фингерпринтинга
К важными задачам коллекционной работы относится идентификация и паспортизация культур микроорганизмов, которые необходимы для безопасного использования микробиологических ресурсов в биотехнологической отрасли (включая растениеводство, животноводство и пищевую промышленность), а также защиты авторских прав на коммерческие штаммы. Для этих целей в настоящее время привлекаются как методы, основанные на изучении физиолого-биохимических свойств штаммов, так и современные молекулярно-генетические методы, например BOX, ERIC, REP-PCR и AFLP-фингерпринтинг (1, 2). Различные варианты фингерпринтин-га основаны на изучении геномной ДНК микроорганизмов для выявления индивидуальных особенностей штаммов, которые могут быть использованы при создании штамм-специфичных паспортов. AFLP-фингерпринтинг (amplified fragment length polymorphism) — один из наиболее перспективных приемов молекулярно-генетической паспортизации микроорганизмов. Метод заключается в анализе полиморфизма длин рестрицированных и ам-плифицированных фрагментов ДНК (3, 4). Его преимущество — очень высокая чувствительность, которая позволяет генерировать индивидуальные профили штаммов и различать их в пределах одного вида. Ранее с помощью AFLP-фингерпринтинга были успешно проведены исследования генетических различий между близкородственными штаммами клубеньковых бактерий, относящихся к разным родам (5-7).
В связи с этим наша цель заключалась в разработке методики генетической паспортизации штаммов, депонированных в Ведомственной коллекции полезных микроорганизмов сельскохозяйственного назначения Россельхозакадемии, с помощью AFLP-фингерпринтинга.
Методика . Объектами исследования были 16 практически ценных штаммов из коллекции ВКСМ: Rhizobium leguminosarum (348, 700, 261 и
Работа выполнена при поддержке Министерства образования и науки РФ в рамках ФЦП «Исследования и разработки по приоритетным направлениям развития научно-технического комплекса России на 2007-2013 годы» (Государственный контракт № 16.518.11.7095).
712), Rhizobium galegae 912, Bradyrhizobium japonicum 630, Bradyrhizobium sp. 820, Bacillus thuringiensis (626, 634, 603, 640 и 642), а также штаммы Lactobacillus plantarum (616, 621, 631 и 613). Штаммы клубеньковых бактерий культивировались при 28 ° C на маннитно-дрожжевом агаре (YMA), Bacillus thuringiensis — на мясопептонном агаре (МПА), молочнокислые бактерии — на жидком сусле (8).
Общую ДНК клубеньковых бактерий выделяли по следующей методике: 1,5 мл ночной культуры клеток ризобий центрифугировали при 14000 об/мин в течение 2 мин. Надосадочную жидкость удаляли, а клетки ресуспендировали в 500 мкл буфера TE (Трис-HCl — 10 ммоль/л, EDTA — 5 ммоль/л, pH 8,0). К суспензии добавляли лизоцим (1 мг/мл), инкубировали 5 мин при комнатной температуре, затем вносили SDS до концентрации 0,5 % и протеиназу К до концентрации 0,05 мг/мл и инкубировали при 37 ° C в течение 1 ч. Экстракцию проводили смесью фенола, хлороформа и изоамилового спирта (24:24:1). ДНК осаждали двумя объемами этанола 5 мин при комнатной температуре. Раствор центрифугировали 2 мин при 14 000 об/мин и растворяли осадок в 100 мкл дистиллированной воды. В случае выделения ДНК из бактерий рода Bacillus и Lactobacillus вводили стадию предварительной обработки протеиназой К в концентрации 0,05 мг/мл при 60 ° C в течение 1 ч, при необходимости для разрушения клеток суспензию встряхивали со стеклянными шариками в гомогенизаторе FastPrep24 («MP Biomedicals», США) при максимальной мощности в течение 1 мин. Окончательную очистку проводили, как описано выше.
Полученную геномную ДНК (50 нг) использовали для одновременной реакции рестрикции и лигирования. В состав реакционной смеси входили по 2,5 ед. рестриктаз MseI и EcoRI («MBI Fermentas», Литва), 1 ед. лигазы фага Т4 («MBI Fermentas», Литва), два олигонуклеотидных адаптера — для сайта EcoRI (adEco1 CTCGTAGACTGCGTACC и adEco2 AAT-TGGTACGCAGTCTAC) и для сайта MseI (adMse1 GACGAGAGTCCTG-AG и adMse2 TACTCaGgACTCAT) в количестве 5 пмоль каждого. Реакцию проводили в буфере для лигазы («MBI Fermentas», Литва) при 37 ° C в течение 16 ч.
В финальной амплификации, результатом которой были геномные фингерпринты, в качестве матрицы использовали 1 мкл реакционной смеси, полученной на предыдущей стадии, и селективные праймеры (по одному для каждого адаптера, флуоресцентно меченного красителем FAM): Mse_a GA-TGAGTCCTGAGTAAA, Mse_cg GATGAGTCCTGAGTAACG или Mse_ca GATGAGTCCTGAGTAACA — для сайта MseI; Eco_0 GACTGC-GTACCAATT или Eco_a GACTGCGTACCAATTCA — для сайта EcoRI (по 10 пмоль каждого). Для поиска оптимального сочетания испытывали все возможные комбинации MseI/EcoRI селективных праймеров. Предварительную оценку результата проводили в агарозном 3 % геле, финальную — в условиях автоматического капиллярного электрофореза на генетическом анализаторе ABI 3500xl («Applied Biosystems», США). В смесь для электрофоретического разделения добавляли также интервальный маркер молекулярной массы GeneScan-600 LIZ Size Standard («Applied Biosystems», США).
При сопоставлении фингерпринтов использовали программу FPQuest («Bio Rad», США). Исходным материалом для анализа служили файлы, полученные после электрофоретического разделения фрагментов и содержащие кривые, которые соответствовали фрагментам AFLP (FAM) и стандарту молекулярной массы (LIZ). Файлы предварительно экспортировали в TIFF-формат.
Степень сходства между фингерпринтами оценивали по корреля- ции Пирсона, ориентированной скорее на поиск общего сходства между кривыми, чем на поиск фрагментов одинакового размера.
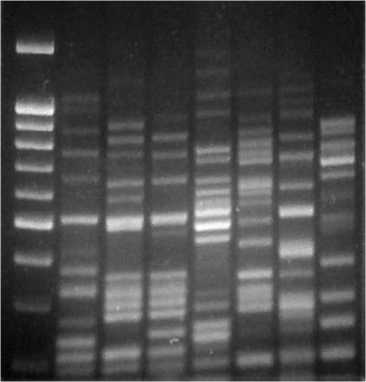
Рис. 1. Предварительный электрофорез в 3 % агарозном геле AFLP-фрагментов ДНК ризо-бий, полученных с использованием селективных праймеров Mse_ca/Eco_a.
Резуёътаты . Из всех проанализированных штаммов мы выделили геномную ДНК, концентрация и степень очистки которой были достаточными для проведения AFLP. Реакции рестрикции и лигирования с адаптерами дали отличный результат, так как при использовании рестрик-ционно-лигазной смеси в качестве матрицы на завершающем этапе AFLP-ПЦР для всех проанализированных микроорганизмов получили высокоспецифичные профили. В результате изучения разных комбинаций селективных праймеров была отобрана пара Mse_ca/Eco_a как дающая оптимальное соотношение количества и специфичности фрагментов (рис. 1).
Обработка полученных данных в программе FPQuest позволила эф фективно выравнять фингерпринты, вычислить степень их родства и провести кластерный анализ, включающий статистическую поддержку кластеризации. На первом этапе была построена дендрограмма родства, объеди няющая все полученные данные, включая различные штаммы и разные объемы смеси фрагментов, использованные при электрофорезе (1; 0,5; 0,25 или 0,1 мкл) с целью подбора оптимального соотношения для обеспечения эффективного разделения и элиминации эффектов, связанных с перегрузкой или недостаточным количеством внесенного материала (рис. 2).
Анализ полученных данных показал, что за исключением штаммов, имеющих высокий уровень сходства (штаммы 621, 616, 631 и 613 Lactobacillus ; 626/634 и 640/642 Bacillus thuringiensis ), фингерпринты группируются строго по штаммам, демонстрируя очень высокое сходство между профилями, соответствующими разным количествам AFLP-смеси и принадлежащим одному и тому же штамму. На основании сопоставления результатов было продемонстрировано, что в проводимом эксперименте оптимальное для нанесения в генетический анализатор количество соответствует 0,1 мкл смеси AFLP. Поэтому для финального сравнения выбрали именно эти образцы с наименьшей концентрацией (рис. 3). Их анализ выявил очевидные различия в наборах фрагментов ДНК, что свидетельствует об очень высокой чувствительности метода, который позволяет получать уникальные профили для каждого штамма и дискриминировать их в пределах одного вида. Тем не менее, несмотря на очень высокую специфичность метода, кластерный анализ AFLP-профилей позволяет достаточно четко группировать штаммы в соответствии с их филогенетическим родством. На дендрограмме (см. рис. 3) штаммы ризобий (348, 912, 630, 820, 700, 261 и 712), штаммы Bacillus (626, 634, 603, 640 и 642), а также штаммы Lactobacillus (616, 621, 631 и 613) образуют обособленные группы. Среди проанализированных клубеньковых бактерий пять штаммов — 348 ( Rhizobium leguminosarum bv. trifolii ), 912 ( Rhizobium galegae ), 630 ( Bradyrhizobium japonicum ), 820 ( Bradyrhizobium sp.), 700 ( Rhizobium leguminosarum bv. phaseoli ) оказались вне кластеров (уровни сходства менее 30 %) . Другие два штамма
Pearson correlation (Opt: 1,00%) [0,0 %-100,0 %]
ABI
ABI
lllllllllllllll llllllll
■ill пип и mi
11 III
11 III
I II
I II
I II
I II I I I I I
Illi I Illi lllll
lllll
I
ii i
I I
d
{
II lllllllllllllllllll i iiiiiii min ill..... i iiiiiiiiiiiiiiiini i i пни и mi ii mi i
I II
II II III
Illi
i mil и и i hi
III II llll 11II II
I
III
1111111*11111111
I lllll.............I I lllll llllllll Illi
Illi
I
I
II
I I
и
II II llll
II IIII
II
II Illllll
II I I I I I
III
626-3 6264
6344 634-1 634-2 626-1 626-2 634-3 603-1 603-2 603-3 6034
6404 6424 642-2
640-2
640-3
III
III
III
ISHII! I III llllll lllllllllllll 11II III
II11III ......
Illllll II
■III III
I
II
iiiiiiiniiiieio и i
lllll
lllllllllllllllllll

■III HI
■lllll III ■llllll II11
I II
IBII
lllll I ■ I II II I II I I I I
II Illllll
II Illllll
1 llllll
I III
642-3
642-1
I I
I III
II llll ■ III
llllll I llllll I llll I
II l■llll 111
III !■—llll II llllllll III
■
ii
III llllll*
ill ■пинmini
Hinn iiiiiiii
inn i
llllll I «III
III.............. IIIllllIII..... lllllllllllllll llll llll llll
Illi II lllll I 111 III llllll
III I lllll I II II Illi
I I
I I
II II
i
11 11
I I
ii
III
I II
I
in ini
i hi ii in
I
in и
I 11 IIIIII
I I I llll I
II 111
llllll lllll I II I Illi I
II I III
ii 11 ini mm ini in i пин и num 11 ш и i n i inni и mi inimii i mini 11in и in
in i i и ini in inn mini 11 in
I I I II II I I 11 II ■ I llllllll I llllll II III I
i in
■i nimi I lllll II I II
II
III III lllllllllllll I llll II I llll II I
I I IIllll I I llll I II I
I 111
I lllllllllllllll IIIHIIIIII llllll II 11
III III IIIHIIIIII lllllllllllll lllll
I 1 1
llllll II Illi IIIHIIIIII I Illi llllll IIIIIIlllllIII
I lllll I lllll II III II llllllll II Illi llll III llllllll II lllllllllllllllll 11II llll II I
III
d
II
mi mi i huh iniiiiiiii i in ini i ii ii min ini
III IIIllllllI III llllll III II I II I llllll
III
Illi IIIJ lllllllllllllll I III Illi II I II II lllll
II
d
lllll
II 111
I llll
iiii Mill
I И 1 1
lllll llllll
Illi
Illi
III
Illi Illi
Illi I
II II
I II I
III llll
III
III
III
I II lllll I Illi I
min i i imui i
Mil Illi
llll llllllll
III lllll
I III
I III
II
II
640 1 621-1 621-3 613-1 613-3 616-1 616-2 613-2 621-2 631-2 631-3 631-1 6134 6314 616-3 6164 6214 820-1 820-3 8204 820-2 912-1 912-2 912-3 9124 348-2 348-3 348-1 3484 630-1 630-3 6304 630-2 700-2 700-3 700-1 7004 261-1 261-3 2614 261-2 712-1 712-3 712-2
Рис. 2. Сопоставление всех данных (все штаммы микроорганизмов и все количества), полученных при разделении AFLP-фрагментов на генетическом анализаторе (ABI 3500xl, «Applied Biosystems», США): 1 - 1 мкл, 2 — 0,5 мкл, 3 — 0,25 мкл, 4 — 0,1 мкл.
ризобий (261 и 712 Rhizobium leguminosarum bv. viciae ), как и штаммы Bacillus и Lactobacillus , могут быть отнесены к отдельным группам, поскольку степень сходства более 50 % достаточна для статистически достоверного
разделения кластеров (9, 10).

IIIIIDIIIIIIIIIIIIIIIIIII шнiiiши । mu iiiiiiiiiiiiiiiiiiiiiiniii mu min iiiiii in min нт и mi inn iiiiiniiiiiiiiiiiiiiii iiiiiiiiiiiiiiiiiiiiii iiiiiiiiiiiiiii in mi iiiiiiiiiiiiiiiiiiiiii
348-4 912-4 630-4 820-4 700-4 261-4 712-4 626-4 634-4 603-4 640-4 642-4 616-4 621-4 631-4 613-4
Pearson correlation (Opt: [0,0 %-100,0 %] ABI
1,00%) ABI
Рис. 3. Сопоставление данных AFLP-фингерпринтинга, соответствующих внесению 0,1 мкл смеси, для всех проанализированных штаммов.
Таким образом, метод AFLP-фингерпринтинга продемонстрировал высокую разрешающую способность при проведении как внутривидовой, так и межвидовой дифференциации генотипов. Метод характеризуется высокой воспроизводимостью, наличием ряда эффективных подходов к анализу полученных данных и может с успехом применяться в растениеводстве, ветеринарии и в пищевой промышленности для молекулярно-генетической характеристики практически ценных штаммов микроорганизмов. Результаты исследования будут использованы для стандартизации процедуры проведения комплексной доказательной паспортизации штаммов сельскохозяйственных микроорганизмов, депонированных в Ведомственной коллекции полезных микроорганизмов сельскохозяйственного назначения Рос-сельхозакадемии (ВКСМ).


