Сравнительный анализ генных карт Bos taurus L. и Capra hircus L
Автор: Эрнст Л.К., Кленовицкий П.М., Багиров В.А., Иолчиев Б.С., Зиновьева Н.А., Калашников В.В., Фисинин В.И., Жилинский М.А.
Журнал: Сельскохозяйственная биология @agrobiology
Рубрика: Генные карты и молекулярная структура генома
Статья в выпуске: 2 т.48, 2013 года.
Бесплатный доступ
С использованием банка данных по генетическим картам животных и разработанного программного обеспечения проведено сравнение генных порядков у двух представителей семейства Bovidae — Bos taurus L. и Capra hircus L. Показано высокое сходство генных порядков гомеологичных хромосом у сравниваемых видов, за исключением хромосом 9-й и 14-й пар.
Дивергенция, геном, генетические карты, гомеология, кариотип, хромосомы, хромосомные карты
Короткий адрес: https://sciup.org/142133395
IDR: 142133395 | УДК: 636.082.12:599.735.51/.52:575.1:576.3
Comparative analysis of genetic maps of Bos taurus L. and Capra hircus L
With the use of data base of genetic maps of animals and developed software the authors have made comparative analysis of gene orders in two representatives of Bovidae family, Bos taurus L. and Capra hircus L. It was shown the high similarity of gene orders of homeological chromosomes in compared species, with the exception of 9th and 14th chromosome pairs.
Текст научной статьи Сравнительный анализ генных карт Bos taurus L. и Capra hircus L
Изучение филогенеза животных невозможно без углубленного использования достижений современной биологии, в частности знаний об особенностях организации и функционирования хромосомного аппарата. В решении вопросов систематики и филогенеза млекопитающих большую роль играют цитогенетические методы (1-3). В последние десятилетия изучение хромосомных наборов применяется и в прикладных исследованиях (4, 5), в том числе в работах по сохранению и рациональному использованию генофонда животных (6-10). В эволюционной генетике нашел широкое приложение анализ тонкой структуры хромосом. Одним из подходов при изучении гомеологии хромосом, а также их отдельных участков у различных видов млекопитающих служит сравнение дифференциальной ис-черченности.
Ряд работ посвящен анализу цитогенетического сходства и эволюции кариотипов (11-13). Как отмечают А.С. Графодатский и Л.С. Битуева (12), гомеологичные участки хромосом идентифицируются по характеру рисунка тем чаще и надежнее, чем меньше сравниваемые кариотипы перестроены относительно друг друга. За редким исключением гомеология хорошо прослеживается при сравнении видов внутри рода или близких родов. Иногда удается с достаточной степенью надежности идентифицировать ее в пределах семейства.
В последнее время для оценки сходства геномов широко используются различные молекулярно-генетические маркеры (14-19). Однако наиболее точным критерием сходства (тождественности) геномов может служить лишь тот факт, что хромосомы или их фрагменты содержат одинаковые нуклеотидные последовательности, расположенные в одном и том же порядке, независимо от аллелизма.
Имеются исследования, посвященные сравнению генного состава отдельных хромосом у разных видов (20-28), также известны работы по анализу филогенеза на основе сопоставления генных карт (29-32). При сравнении дифференциальной структуры хромосом выявлены пути цитогенетической дивергенции у разных видов овец (33-37). Изучение генных порядков у Bos taurus L. и Ovis aries L. позволило более детально проанализировать характер дивергенции их кариотипов (32). Однако во всех этих работах объектом исследованиях были виды с выраженными цитогенети- ческими различиями.
В представляемой работе нами проведено сравнение генных карт у двух родственных видов из семейства Bovidae — Bos taurus L. и Capra hircus L., имеющих сходные хромосомные наборы, с целью поиска различий в организации геномов у этих таксонов на уровне генных порядков.
Методика . Исследования выполняли с привлечением собственного банка данных о хромосомной локализации маркеров у B . taurus L. и C . hircus L., включающего обобщенную информацию из баз данных NAGRP (National Animal Genome Research Program, США) (38), INRA (39, 40) и содержащего сведения о локализации соответственно 28 282 и 708 маркеров. При этом для 249 маркеров известна хромосомная локализация у обоих видов. Кроме того, использовали материалы A. Eggen и R. Fries (41), J.J. Lauvergne с соавт. (42), J. Maurico с соавт. (43) и Bovine genome DataBase (44). Анализ генных карт проводили по алгоритмам, описанным нами ранее (28, 29).
Для цитогенетической характеристики сравниваемых видов из 72часовой культуры периферических лимфоцитов, стимулированной конка-навалином А («Панэко», Россия) в дозе 10 мкг/мл, готовили препараты хромосом. Культивирование лимфоцитов, подготовку и обработку препаратов хромосом проводили по общепринятой методике (45) с внесенными нами модификациями (46).
Результаты исследования документировали с помощью цифровой видеокамеры КС-583С («Digital», Tawan) и пакета программ, совместимых с Windows. Обработку изображений и кариотипирование осуществляли по описанной ранее методике (46).
Результаты . Для видов, образующих семейство Полорогие ( Bovidae ), характерна высокая цитогенетическая вариабельность. Полагают, что исходный кариотип полорогих содержал 60 хромосом, включая 29 пар одноплечих аутосом. Расхождение ветвей, давших начало современным представителям этого семейства, произошло 15-20 млн лет назад. На основании сопоставления хромосомных наборов у различных представителей полорогих принято считать, что эволюция кариотипов в этом семействе происходила главным образом в результате центрических слияний (47). Изменение морфологии половых хромосом у полорогих связывают с перицен-трическими инверсиями.
Из современных полорогих к предковой форме кариологически наиболее близки представители рода Capra , обладающие хромосомной мо-номорфностью (3, 45, 48, 49). Среди них наиболее полно изучен кариотип у C . hirous (50-53). Диплоидное число хромосом у козы равно 60. Кариотип этого вида включает 29 пар акроцентрических аутосом. X-хромосома представляет собой крупный акроцентрик, тогда как Y-хромосома мета-центрична и относится к наиболее мелким в наборе (рис. 1, А). Точная идентификация хромосом, за исключением Y-хромосомы, возможна лишь с применение дифференциального окрашивания. Из одомашненных представителей полорогих по числу и морфологии хромосом к C . hirous наиболее близок B . taurus (см. рис. 1, Б).
Диплоидное число у обоих видов равно 60, а число плеч аутосом — 58. Характер рисунка гомологичных хромосом, исключая 9-ю и 14-ю пары, у обоих видов идентичен (4, 5). У B. taurus и C. hirous для большинства хромосом характерно относительно равномерное чередование светлых и темных блоков по всей длине. Морфологические различия имеют место в организации женских половых хромосом: у B. taurus Х-хромосома — крупный метацентрик. Различие в морфологии женских хромосом у этих видов обусловлено перицентрической инверсией (54).
А

Рис. 1. Кариотип у Capra hircus L. (самец) (А) и Bos taurus L. (самец) (Б). Окраска по Гимзе, увеличение *100.
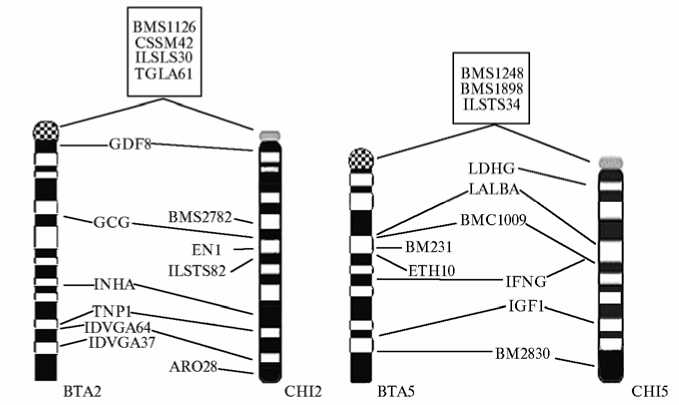
В таблице представлены данные о соответствии генного состава хромосом B. taurus и C. hircus., в частности сведения 95 маркеров первого и 154 маркеров второго типа. Для 22 пар хромосом у анализируемых видов отмечалось полное совпадение их генного состава. В эту группу входят хромосомы 2-5-й, 9-13-й, 15-19-й, 21-25-й, 28-й, 29-й пар и половые хро- мосомы. В качестве примера на рисунке 2, А приведены генные карты 2-й и 5-й пар хромосом крупного рогатого скота и козы.
Соответствие генного состава хромосом у Capra hircus L. (самец) и Bos taurus L. (самец)
|
C . hircus L. |
B . taurus L. |
|
|
№ пары хромосом | |
плечо |
№ пары хромосом и число генов |
|
1-я |
q |
1q (23: 9, 14); 16q (1: 0, 1) |
|
2-я |
q |
2q (14: 6, 8) |
|
3-я |
q |
3q (10: 2, 8) |
|
4-я |
q |
4q (9: 3, 6) |
|
5-я |
q |
5q (11: 4, 7) |
|
6-я |
q |
6q (5: 3, 2) |
|
7-я |
q |
7q (5: 3, 2) |
|
8-я |
q |
8q (7: 2, 5); 11q (1: 0, 1) |
|
9-я |
q |
9q (6: 1, 5) |
|
10-я |
q |
10q (10: 4, 6) |
|
11-я |
q |
11q (16: 5, 11) |
|
12-я |
q |
12q (9: 3, 6) |
|
13-я |
q |
13q (6: 3, 3) |
|
14-я |
q |
9q (3: 0, 3); 14q (8: 3, 5) |
|
15-я |
q |
15q (7: 3, 4) |
|
16-я |
q |
16q (9: 1, 8) |
|
17-я |
q |
17q (7: 2, 5) |
|
18-я |
q |
18q (10: 6, 4) |
|
19-я |
q |
19q (4: 1, 3) |
|
20-я |
q |
1q (1: 1, 0); 9q (1: 0, 1); 20 (6: 0, 6) |
|
21-я |
q |
21q (6: 2, 4) |
|
22-я |
q |
7q (1: 0, 1); 22q (7: 3, 4) |
|
23-я |
q |
23q (5: 2, 3) |
|
24-я |
q |
24q (6: 0, 6) |
|
25-я |
q |
25q (8: 2, 6) |
|
26-я |
q |
14q (1: 0, 1); 26q (4: 1, 3) |
|
27-я |
q |
17q (1: 1, 0); 26q (1: 0, 1); 27q (4: 0, 4) |
|
28-я |
q |
28q (5: 0, 5) |
|
29-я |
q |
29q (4: 0, 4) |
|
X |
X (5: 3, 2) |
|
|
Y |
Y (1: 1, 0) |
|
Примечание. В скобках приведено общее число локусов, известных у C . hircus L., в том числе соответственно структурных генов и ДНК-маркеров.
Необходимо отметить, что для части использованных в представляемой работе генетических маркеров, общих для крупного рогатого скота и козы, точная локализация на хромосомах пока не определена.
По 7 хромосомным парам наблюдали разную степень несоответствия генного состава у C . hircus и B. taurus . Наиболее значительные разли-
А
Б
В
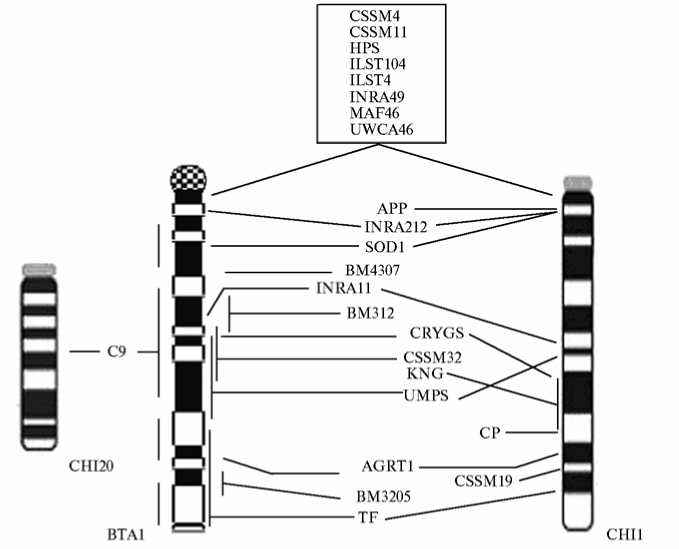
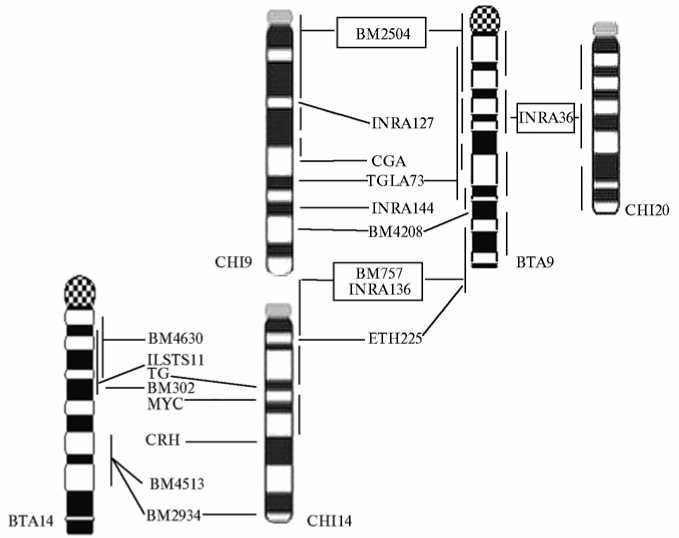
Рис. 2. Сравнение генных карт 2-й и 5-й пар хромосом у Capra hircus L. (CHI2, CHI5) и Bos taurus L. (BTA2, BTA5) (А) , 9-й и 14-й пары у C . hircus (CHI9, CHI14) и B . taurus (BTA9, BTA14) (Б) , а также 1-й пары у C . hircus (CHI1) и B . taurus (BTA1) (В). В рамке приведены обозначения генов, точная локализация которых у обоих видов не известна. Ген С9 и маркер INRA36 локализованы на 20-й хромосоме козы.
чия генных порядков у этих видов выявили между хромосомами 14-й пары (см. рис. 2, Б).
Оказалось, что из 11 генетических маркеров на хромосоме 14-й пары у козы 8 расположены на BTA14 и 3 — на BTA9. У B. taurus хромосо- ма 9-й пары содержит 10 маркеров, локализация которых известна и у C. hircus, из них 6 находятся на CHI9, 3 — на CHI14 и 1 — на CHI20. К сожалению, точная локализация генетических маркеров на BTA9 не выявлена, что пока не позволяет определить характер изменения генных порядков в этих хромосомах. Дополнительно ситуация осложняется тем, что для BTA14 в настоящее время неизвестны реперные гены, локализованные вне CHI14.
Хромосома 1-й пары козы по генному составу соответствует BTA1. Но помимо маркеров, расположенных на CHI1, на BTA1 был выявлен ген 9-го компонента комплемента ( С9 ), находящийся у козы на хромосоме 20-й пары (см. рис. 2, Б).
Хромосомы 8-й и 22-й пар у крупного рогатого скота по большинству маркеров соответствовали CHI8 и CHI22. Но на CHI8 находился также ДНК-маркер HEL13, локализованный у B . taurus на BTA11, а на CHI22 выявили микросателлитный маркер BM7160, сцепленный с BTA7.
По аналогии при сравнении генных порядков в хромосомах 26-й пары было установлено, что CHI26 и BTA26 имеют 4 общих маркера. Помимо этого, на BTA26 присутствовал маркер CSSM43, ассоциированный с CHI27, а на CHI26 — BM4305, сцепленный с BTA14.
Из 8 маркеров, обнаруженных на хромосоме 20-й пары у козы, 6 присутствовали на BTA20, а маркеры C9 и INRA36 имелись соответственно на BTA1 и BTA9. У козы с хромосомой 27-й пары были ассоциированы 6 маркеров, у B . taurus 4 из них локализовались на BTA27, а ген фактора свертываемости 11-F11 и микросателлит CSSM43 — соответственно на хромосомах 17-й и 26-й пар.
Таким образом, у сравниваемых видов организация генных порядков характеризуется высокой степенью сходства. Однако в процессе дивергенции их кариотипов имел место обмен генетическим материалом между негомологичными хромосомами. Классический цитогенетический анализ не позволяет вскрыть все тонкости этого процесса, в связи с чем даже при сравнении родственных видов необходимо изучать организацию их геномов на уровне генных карт.


